4TY_wgMLST
Introduzione
L'analisi 4TY_wgMLST esegue il "whole genome Multi-Locus Sequence Typing" (wgMLST) in silico per le specie batteriche Campylobacter jejuni e Campylobacter coli. A differenza del protocollo cgMLST (core genome MLST), la caratterizzazione avviene sul genoma completo (whole genome).
Lancia analisi 4TY_wgMLST
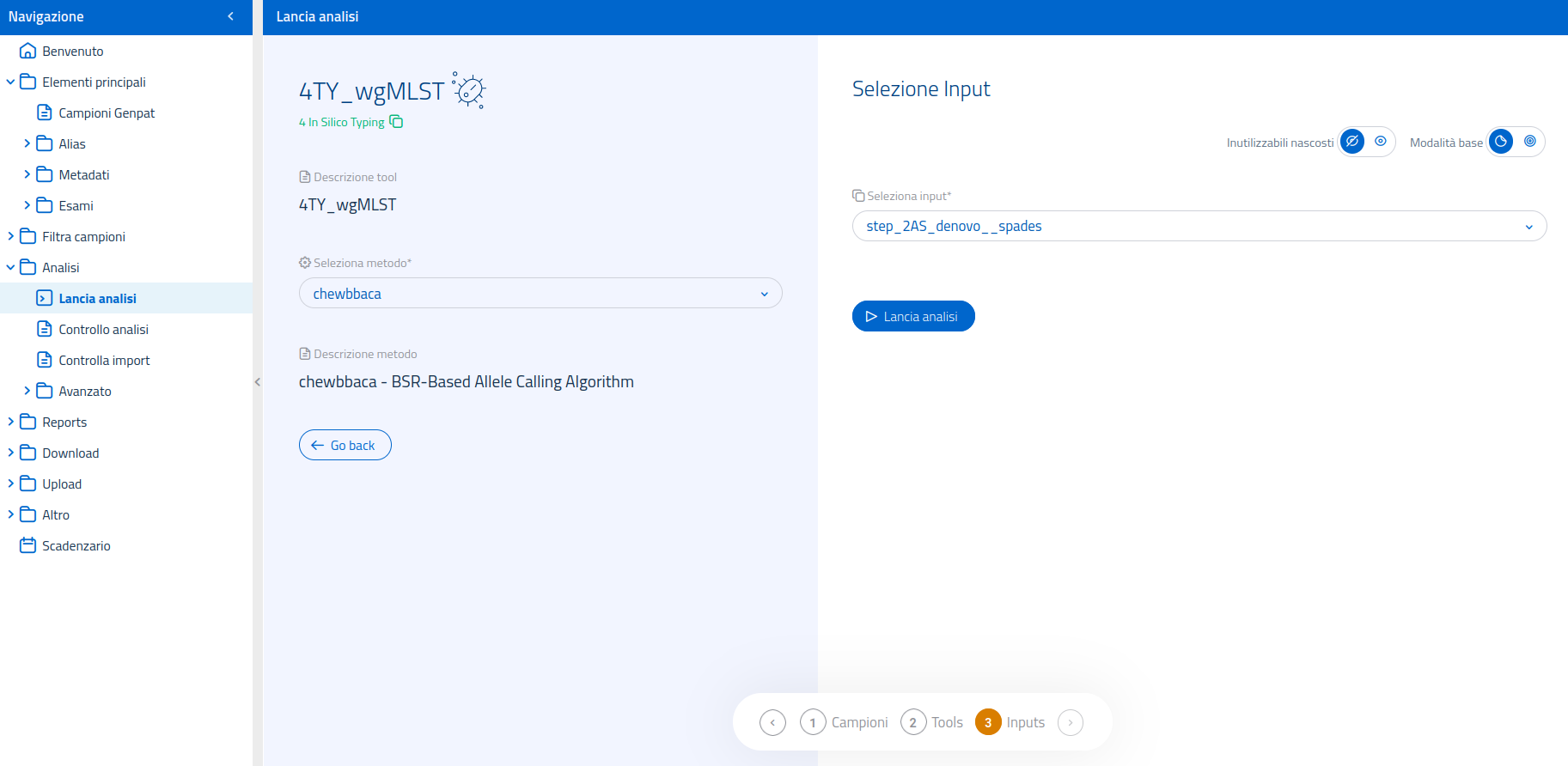
Una volta selezionata l'analisi 4TY_wgMLST nella pagina dedicata al lancio di analisi, sarà possibile selezionare il software bioinformatico ("metodo") da usare tra quelli disponibili per l'analisi. L'unico metodo utilizzabile per questo accertamento è chewBBACA - BSR-Based Allele Calling Algorithm.
Nota: Sono disponibili schemi per wgMLST solo per Campylobacter jejuni e Campylobacter coli. Il lancio dell'analisi su un altro microrganismo, per cui non sia presente lo schema wgMLST, comporterà il fallimento della run.
L'interfaccia per la selezione dell'input mette a disposizione la modalità di selezione input avanzata, per permettere l'utilizzo di input processati da metodi diversi, usati a monte nel flusso di analisi.
I possibili input possono provenire da:
- step_2MG_denovo
- step_2AS_denovo
- step_2AS_mapping
- step_2AS_import
Sarà necessario specificare le sequenze di input - provenienti da un assembly de novo o da un mapping - e indicare il genoma reference utilizzato per il mapping, se quest'ultimo viene selezionato come input.
Una volta lanciata l'analisi, la pagina genererà un link alla sezione Controllo analisi, per permettere di visualizzare lo stato del processo. L'utente verrà notificato dal sistema sia una volta lanciata con successo l'analisi, sia al termine dell'esecuzione.
Cartella dei risultati
Per consultare la guida sul download dei file dalla piattaforma si faccia riferimento all'apposita pagina.
La cartella dei risultati, Result folder, è accessibile cliccando sul link presente all'interno della scheda dell'analisi, nella sezione Dati risultato. All'interno della conseguente cartella results, è possibile trovare 3 sotto-cartelle:
- meta: (metadati) in cui vengono salvati i file di log e di configurazione del processo eseguito;
- qc: (quality check) in cui si trovano i file del controllo qualità. Anche in questa cartella sono presenti le cartelle meta e result. Per questa analisi, il controllo qualità viene effettuato da Quast;
- result: in cui sono salvati i file con i risultati prodotti dall'analisi.
Per la chiamata allelica con chewBBACA i risultati verranno forniti con codifica disponibile secondo 3 diversi schemi:
- schema IZS: ogni allele è identificato da un ID numerico progressivo. L'assegnazione dell'ID avviene considerando tutti i loci, quindi la numerazione NON ricomincia da 1 ad ogni nuovo locus.
- schema MD5: ogni allele è identificato da un codice alfanumerico di 16 caratteri (MD5), ottenuto applicando una funzione di "hash" alla sequenza stessa dell'allele; il che lo rende interscambiabile con altri metodi.
- schema CRC32: controllo basato sul Cyclic Redundancy Check (CRC). Ad ogni allele è assegnato un codice numerico di controllo (check value) determinato dal resto della divisione polinomiale del blocco di dati. Tale valore è utilizzato nello schema come identificatore dell'allele.
Si noti che il file di esempio "DSXXXXXXXX-DTXXXXXX_ID_chewbbaca_results_ccoli_curated_210722.csv" riportato in tabella potrà riportare come suffisso l'abbreviazione per C. coli o C. jejuni, a seconda della specie analizzata.
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_chewbbaca_new_alleles.txt | sequenza dei nuovi alleli identificati | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_chewbbaca_results_contigsInfo.tsv | informazioni sul contig mappato su ogni locus | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_chewbbaca_results_statistics.tsv | statistiche sul numero di loci con codifica EXC, INF, LNF, PLOT, NIPH, ALM, ASM | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_import_chewbbaca_check.csv | controllo qualità con le informazioni su calledPerc, calledNum, annotated, new, notFound, discarded | cartella: qc > result |
| DSXXXXXXXX-DTXXXXXX_ID_chewbbaca_results_crc32.csv | tabella .csv degli alleli codificati con schema CRC32. Righe: campioni, colonne: loci | cartella "result" |
Per maggiori informazioni sulla codifica dei loci e sui file prodotti da chewBBACA, si invita a consultare la guida ufficiale di chewBBACA.
