Augur
Introduzione
L'integrazione in piattaforma di "Augur: A bioinformatics toolkit for phylogenetic analysis" permette di eseguire la pipeline Augur per produrre un albero filogenetico (con algoritmo Maximum Likelihood - ML), a partire dai file FASTA del mapping o de novo assembly.
Pagina github di Augur: https://github.com/nextstrain/augur/tree/7cb384877cb61e26781dec947f81fee29462c008 Pagina di documentazione ufficiale di Augur: https://docs.nextstrain.org/projects/augur/en/stable/index.html
Una volta calcolato l'albero, è possibile visualizzarlo direttamente in piattaforma (usando Auspice), tramite il sistema integrato di visualizzazione dendrogrammi, accessibile dalla scheda dell'analisi completata.
Lancia analisi Augur
Una volta selezionata l'analisi Augur nella pagina dedicata al lancio di analisi, il sistema passerà ad un'interfaccia di conferma: non vi è necessità di scegliere il tool, in quanto l'analisi è specifica per l'uso di Augur.
L'interfaccia per la selezione dell'input mette a disposizione la modalità avanzata di selezione input, per permettere l'utilizzo di input processati da metodi diversi, usati a monte nel flusso di analisi.
I possibili input utilizzabili per Augur comprendono i risultati di tutte le analisi di mapping o de novo assembly.
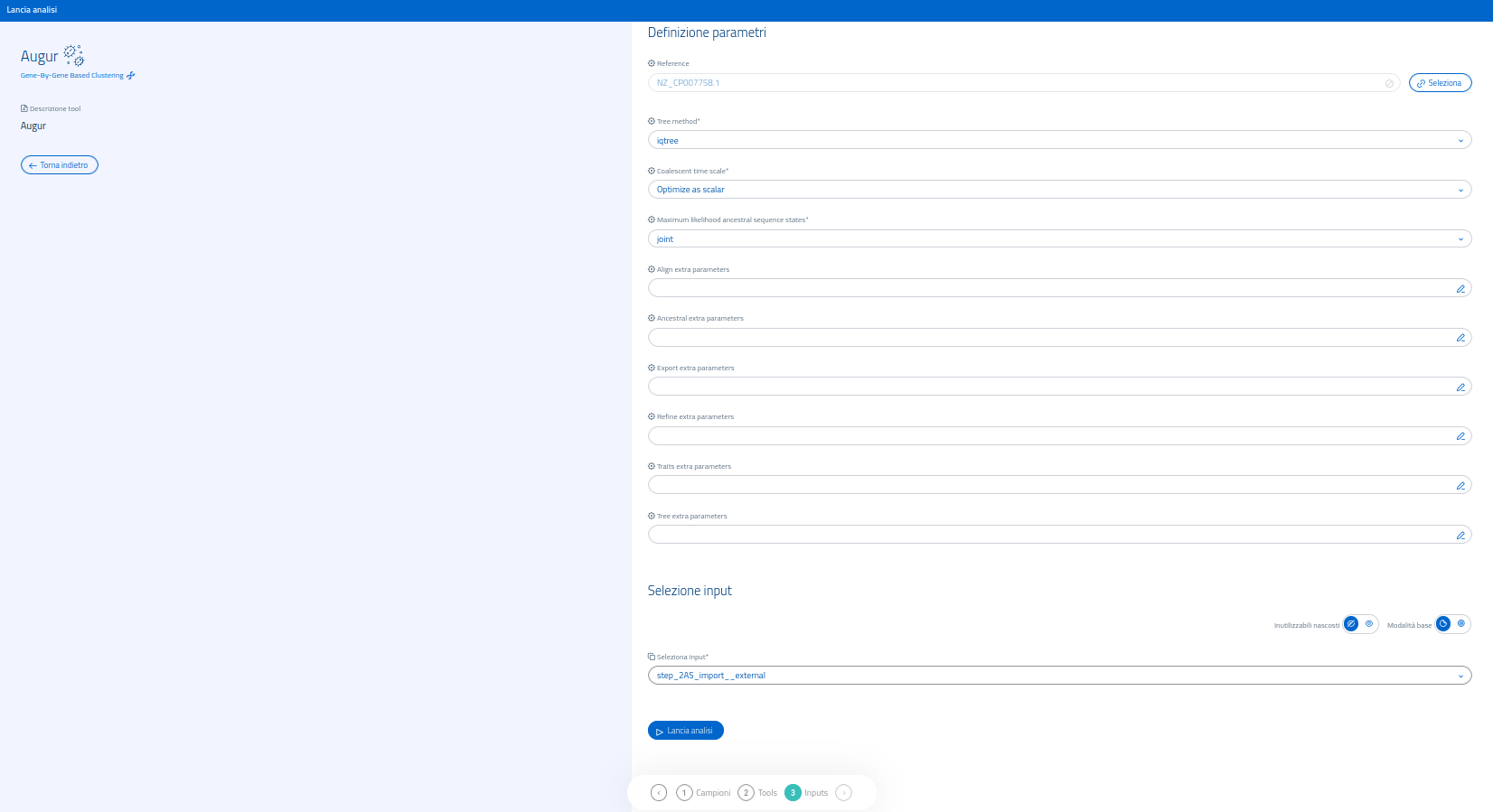
Nella schermata di definizione dei parametri è possibile:
- selezionare il reference da usare come radice dell'albero;
- scegliere il software con cui costruire il file .nwk (iqtree, fasttree o raxm);
- scegliere una modalità per la scala temporale;
- selezionare una modalità per l'algoritmo Maximum Likelihood nel trattare la sequenza ancestrale (reference);
- aggiungere parametri addizionali come testo (i campi riconosceranno i parametri per il lancio del tool da terminale. Consultare la guida ufficiale di Augur per l'elenco dei parametri disponibili).
Una volta lanciata l'analisi, la pagina genererà un link alla sezione Controllo analisi, per permettere di verificare lo stato del processo. Il sistema invierà una notifica all'utente sia quando l'analisi viene lanciata con successo, sia al termine dell'esecuzione.
Nella scheda dell'analisi completata, oltre alla possibilità di esplorare la cartella di output, saranno presenti alcune opzioni come l'accesso diretto ad alcuni dei file di log e metadati, l'apertura del file .nwk e la visualizzazione diretta dell'albero Maximumm Likelihood tramite l'integrazione in piattaforma di Auspice.
Per visualizzare l'albero sarà necessario navigare nella scheda risultato di GrapeTree e selezionare il link ML Tree with Auspice:
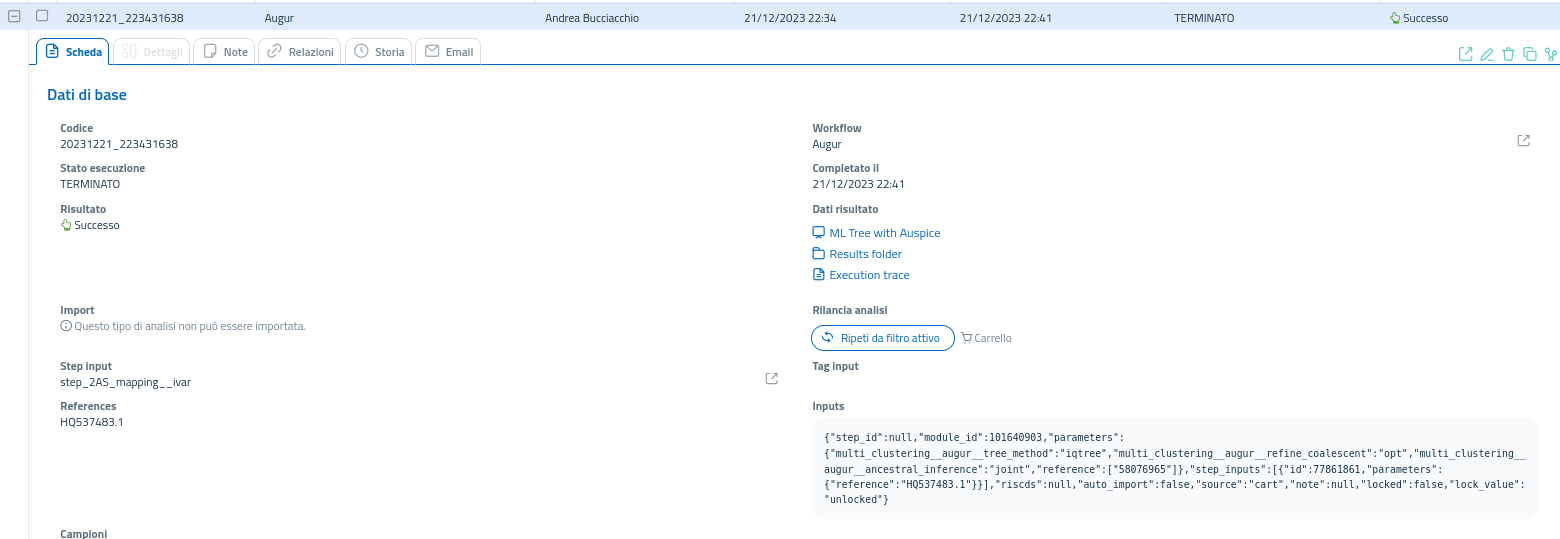
Nota: I risultati delle analisi multi-campione non possono essere importati. Si invita a sfruttare l'apposita funzionalità per la conservazione delle analisi non importabili o, in alternativa, l'opzione per il download diretto del file newick (
.nwk) e del file dei metadati, in modo da poter conservare i file e visualizzare l'albero in qualunque momento, sia all'interno della piattaforma sia attraverso un software esterno.
Cartella dei risultati
Per consultare la guida sul download dei file dalla piattaforma si faccia riferimento all'apposita pagina.
La cartella di output, Result folder, può essere esplorata cliccando sul link presente all'interno della scheda dell'analisi. All'interno della successiva cartella Results vi sono due sotto-cartelle:
- meta (metadati), in cui vengono salvati i file di log e di configurazione del processo eseguito.
- result, in cui sono salvati i file con i risultati prodotti dall'analisi.
La tabella in basso mostra la lista dei principali file di interesse presenti nelle cartelle, insieme ad alcune informazioni utili.
| File | Descrizione | Posizione |
|---|---|---|
| aa_muts.json | file json usato da Auspice per le mutazioni negli amminoacidi | cartella "result" |
| alignment.fasta | FASTA del multiallineamento | cartella "result" |
| augur_metadata.tsv | tabella dei metadati in formato tsv prodotta da Augur | cartella "result" |
| auspice.json | file json usato da Auspice per la costruzione delle corrispondenze tra foglie del dendrogramma e nodi sulla mappa | cartella "result" |
| branch_lengths.json | cartella result | |
| nt_muts.json | file json usato da Auspice per le mutazioni nella sequenza nucleotidica | cartella "result" |
| traits.json | file json usato da Auspice per popolare i campi dei metadati | cartella "result" |
| tree.nwk | file dell'albero in formato .nwk (newick) calcolato con algoritmo Maximum Likelihood | cartella "result" |
| metadata.csv | tabella dei metadati in formato csv | cartella "result" |
Il file in formato nwk contiene tutti i dati dell'albero e può essere visualizzato tramite Auspice o un altro software esterno per la visualizzazione di dendrogrammi.
