GrapeTree
Introduzione
L'analisi GrapeTree costruisce grafici ad albero usando i 2 algoritmi "Minimum Spanning Tree" (MSTree) e "Neighbor Joining" (NJ) a partire dai profili allelici dei campioni forniti, così come identificati nell'analisi cgMLST.
Pagina github di GrapeTree: https://github.com/achtman-lab/GrapeTree
In piattaforma è possibile sia calcolare gli alberi, sia visualizzarli grazie all'integrazione della versione stand-alone del sistema interattivo di visualizzazione di GrapeTree.
Una guida completa all'uso e all'interfaccia del sistema di visualizzazione in piattaforma è disponibile nella pagina dedicata a SPREAD.
Per ulteriori informazioni sul software, si invita a consultare l'articolo e la documentazione ufficiale del sistema EnteroBase, di cui GrapeTree fa parte.
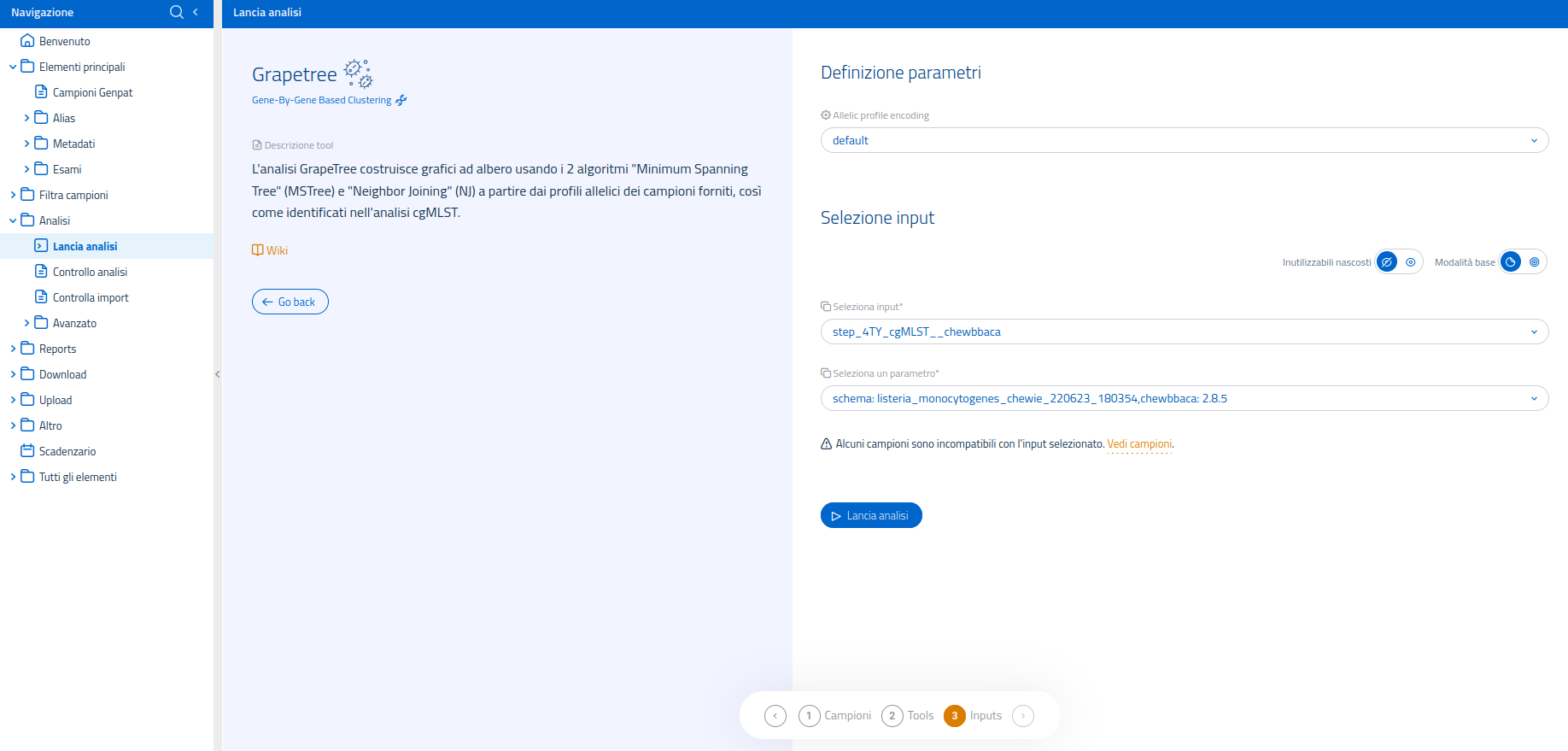
Lancia analisi Grapetree
Una volta selezionata l'analisi Grapetree nella pagina dedicata al lancio di analisi, il sistema passerà ad un'interfaccia di conferma: non sarà necessario scegliere un tool dal momento che le analisi multi-campione usano sempre un software specifico.
L'interfaccia per la selezione dell'input mette a disposizione la modalità di selezione input avanzata, per permettere l'utilizzo di input processati da metodi diversi, usati a monte nel flusso di analisi.
I possibili input utilizzabili per Grapetree sono:
Per entrambi gli input possibili, è necessario che il programma utilizzato, per il calcolo dei profili allelici, sia chewBBACA. Si consiglia, dunque, di prestare particolare attenzione e selezionare tale software per il lancio dell'analisi 4TY_cgMLST o 4TY_wgMLST, se si intende lanciare GrapeTree come analisi a valle.
Nella schermata di definizione parametri è possibile:
- selezionare la codifica: le possibilità comprendono la codifica crc32 e la codifica izsam. La selezione di default corrisponde a crc32;
- specificare lo schema per la specie microbica su cui è stato eseguito 4TY_cgMLST__chewbbaca, se vengono selezionati come input i profili allelici da cgMLST. Il campo è precompilato con lo schema appropriato alla specie batterica i cui codici sono presenti nel carrello, o nel tag attivo, usato per il lancio dell'analisi. Non è pertanto necessario alcun intervento ulteriore, da parte dell'utente.
Nota: di default GrapeTree usa, come input, l'output della versione 2.8.5 del database di ChewBBACA, con codifica crc32. Allo scopo di mantenere retrocompatibilità con gli esami precedenti, rimane possibile eseguire GrapeTree sui vecchi profili calcolati con ChewBBACA 2.8.4; in tal caso è necessario selezionare izsam come codifica.
Si noti che tali associazioni devono essere rispettate affinché l'analisi venga effettuata correttamente. Qualunque altra combinazione comporterà il fallimento dell'analisi.
Si noti inoltre che, ai fini della validità delle analisi effettuate, è necessario usare la versione ChewBBACA 2.8.5.
Una volta lanciata l'analisi, la pagina genererà un link alla sezione Controllo analisi, per permettere di verificare lo stato del processo. Il sistema invierà una notifica all'utente sia quando l'analisi viene lanciata con successo, sia al termine dell'esecuzione.
Nella scheda dell'analisi completata, oltre alla possibilità di esplorare la cartella di output, saranno presenti alcune opzioni come l'accesso ad alcuni dei file prodotti e la visualizzazione diretta degli alberi MSTree e NJ tramite l'integrazione di GrapeTree in piattaforma.
Per visualizzare l'albero sarà necessario navigare nella scheda del risultato di GrapeTree e selezionare il link Minimum Spanning Tree with Grapetree:
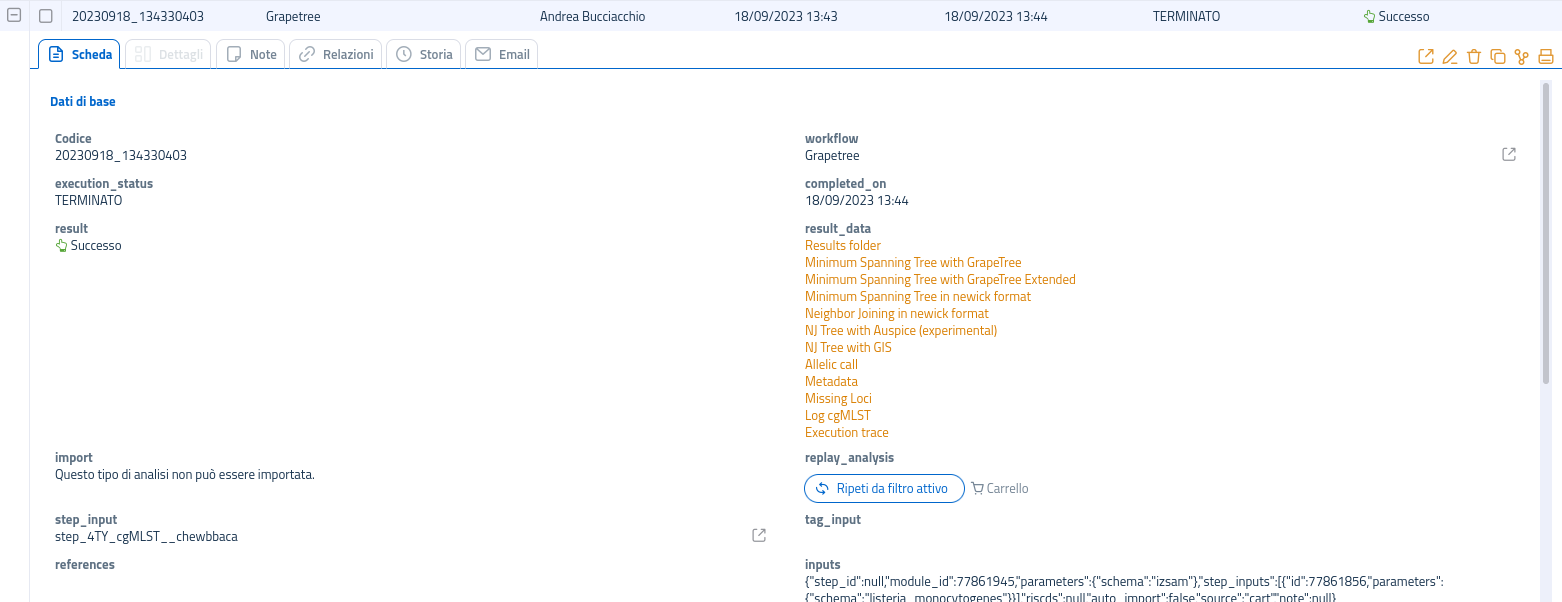
Nota: I risultati delle analisi multi-campione non possono essere importati. Si invita a sfruttare l'apposita funzionalità per la conservazione delle analisi non importabili o, in alternativa, l'opzione per il download diretto del file newick (
.nwk) e del file dei metadati, in modo da poter conservare i file e visualizzare l'albero in qualunque momento, sia all'interno della piattaforma che con un software esterno.
Cartella dei risultati
Per consultare la guida sul download dei files dalla piattaforma si faccia riferimento all'apposita pagina.
La cartella di output, Result folder, può essere esplorata cliccando sul link presente all'interno della scheda dell'analisi. All'interno della successiva cartella Results vi sono due sotto-cartelle:
- meta (metadati), in cui vengono salvati i file di log e di configurazione del processo eseguito;
- result, in cui sono salvati i file con i risultati prodotti dall'analisi.
La tabella in basso mostra la lista dei principali file di interesse presenti nelle cartelle, insieme ad alcune informazioni utili.
| File | Descrizione | Posizione |
|---|---|---|
| cgMLST.nwk | file dell'albero in formato .nwk (newick) calcolato con algoritmo MSTree | cartella "result" |
| cgMLST.tsv | tabella .tsv degli alleli identificati da chewBBACA nel cgMLST (chiamata allelica). Righe: campioni; Colonne: loci. | cartella "result" |
| cgMLST_NJ.nwk | file dell'albero in formato .nwk (newick) calcolato con algoritmo NJ | cartella "result" |
| missing_loci.tsv | elenco dei loci non in comune tra i campioni e quindi scartati per la costruzione dell'albero | cartella "result" |
| cgMLST_dists_matrix.csv | matrice di distanza allelica da cgMLST in formato .csv | cartella "result" |
I file in formato .nwk contengono tutti i dati dell'albero e possono essere visualizzati tramite GrapeTree o un altro software esterno per la visualizzazione dei dendrogrammi.
