FAQ
In questa pagina sono elencate le domande frequenti (FAQ) riguardo l'uso della piattaforma e le corrispondenti risposte. Prima di contattare l'assistenza, per favore controllate se il vostro problema può essere risolto leggendo una delle risposte in questa pagina.
Gestione dati
Come cambio il carattere usato come separatore delle colonne in Excel?
Risposta: Il separatore delle colonne può essere specificato a diversi livelli. Qui sotto riportiamo delle guide per i casi principali:
- per poter modificare il separatore predefinto delle colonne in Excel, è necessario cambiare il carattere da usare come separatore tra le opzioni di sistema Windows;
- per importare in Excel un file con un separatore differente, si può fare riferimento alle diverse guide presenti on-line;
- per dividere le righe di un file di testo usando un altro carattere, sfruttando le funzionalità interne di Excel, è possibile seguire questa guida: https://it.extendoffice.com/documents/excel/1786-excel-split-text-by-space.html;
- se invece si vuole convertire un file si può usare uno strumento online come, ad esempio, quello disponibile a questo link: https://onlinecsvtools.com/change-csv-delimiter.
Nota: I file
.csvche vengono creati per la piattaforma devono avere, come separatore di elenco, il punto e virgola (;), laddove il file che viene creato per il samplesheet necessita, come separatore, la virgola (,).
Non riesco ad esportare una tabella come CSV.
Risposta: L'esportazione in CSV di una tabella della piattaforma viene gestita mediante una finestra popup. Controllare che il browser abbia aperto altre finestre e, in caso contrario, verificare che il browser non abbia bloccato la visualizzazione di popup del sito. Normalmente, quasi tutti i browsers visualizzano un piccolo banner in alto nella pagina, nel quale si chiede all'utente come gestire la richiesta di visualizzazione di un popup.
Si può cambiare il carattere utilizzato come separatore di colonna per l'esportazione dei files CSV?
Risposta: Sì, in piattaforma è possibile modificare il separatore di colonna predefinito, usato per l'esportazione in CSV, nella sezione Preferenze del menù utente: una volta entrati in Preferenze, si può modificare tale carattere nel campo "Separatore CSV". Una volta salvate le modifiche, da quel momento in avanti, quando si esporteranno liste di campioni come CSV, verrà usato il carattere selezionato come separatore.
Carrello e tag
Ricevo un messaggio di errore quando tento di aggiungere al carrello molti campioni.
Risposta: Il carrello può contenere un massimo di 2000 campioni. In caso si debba lavorare su un numero superiore, suggeriamo di creare un tag.
Come faccio a duplicare/clonare un tag?
Risposta: Attiva il tag da duplicare, accedi alla sezione Esplora campioni (dal menu a tendina affianco all'icona del carrello), seleziona quelli di tuo interesse, aggiungili al carrello e crea un nuovo tag a partire dal carrello.
Interfaccia
Come posso visualizzare colonne con ulteriori informazioni nella tabella di un campione?
Risposta: Ulteriori colonne, comprese quelle contenenti informazioni sui risultati (come specie calcolata, quality check, N50, PFGE, percentuale di alleli chiamati, etc.) possono essere visualizzate come descritto nella pagina Wiki "Funzionalità tabelle".
Ulteriori informazioni, non disponibili direttamente nella tabella dei campioni, si possono trovare nella pagina dei "Risultati analisi" (dal menù di Navigazione laterale, Elementi principali > Risultati analisi).
Controllo e visualizzazione dati
Dove trovo i check di un campione?
Risposta: Nel menù di Navigazione laterale sono presenti le tabelle dei Controlli Qualità: Report > Dettaglio > Controllo Qualità principale e Report > Dettaglio > Controlli qualità/Metriche. Usando un filtro, (carrello attivo o tag), si possono filtrare le righe delle tabelle per risalire al/ai campione/i di interesse. Le tabelle dei controlli qualità sono descritte nelle "Pagine dei Controlli Qualità" di questo Wiki.
Dove posso trovare le informazioni sulle raw reads di un campione?
Risposta: Le informazioni sulle raw reads sono visualizzabili nella tabella "Controlli qualità delle read" (Report > Dettaglio > Controlli qualità/Metriche > Controlli delle read). Inoltre, come per i risultati delle analisi, le raw reads dei campioni sono scaricabili tramite le funzionalità di Download. In questo caso il tasto da selezionare è 0sq_rawreads.
Analisi
Come mai GrapeTree non riesce a calcolare il Minimum Spanning Tree?
Risposta: Di solito la causa è che non ci sono alleli di differenza tra i campioni analizzati: GrapeTree non riesce a creare un MST su un dataset con più campioni aventi 0 differenze. Un'altra possibile causa è il numero di campioni: GrapeTree non è in grado di calcolare un albero se si usano solo 2 campioni o meno.
Sui campioni esterni, posso lanciare GrapeTree o devo lanciare prima ChewBBACA?
Risposta: GrapeTree richiede, come input, i profili allelici da ChewBBACA (o altro tool disponibile per 4TY_cgMLST); perchè i profili siano utilizzabili, i risultati di ChewBBACA devono essere stati importati. Sui campioni esterni, quando vengono aggiunti alla piattaforma, le analisi non vengono lanciate automaticamente, (al contrario dei campioni interni). Prima di lanciare GrapeTree su campioni esterni, bisogna assicurarsi che ChewBBACA sia stato lanciato ed i relativi risultati importati. La tabella Elementi principali > Risultati analisi permette di verificare che 4TY_cgMLST sia stato eseguito.
Cosa succede se non conosco l'ospite del mio campione o non voglio farne la deplezione?
Risposta: Se non si desidera (o non è possibile) eseguire il processo di deplezione dell'ospite, si può lanciare direttamente il mapping. I software per la ricostruzione del genoma funzioneranno ugualmente.
ATTENZIONE: Questo approccio è accettabile unicamente se il campione è di ottima qualità e si è certi di ottenere buoni risultati; in caso contrario, i dati saranno inutilizzabili e la piattaforma accumulerà dati di cattiva qualità, danneggiando le analisi future degli utenti.
Come faccio se non conosco il reference migliore per il mio genoma virale?
Risposta: L'analisi 3TX_species, per l'identificazione di specie, può essere lanciata usando il software vdabricate, che identifica il reference migliore nel DB_Virus.
Come posso ottenere informazioni su programmi/opzioni di analisi che sono state svolte automaticamente o da altri utenti del mio gruppo?
Risposta: Se un'analisi è stata eseguita e importata, i risultati (report e QC compresi) sono scaricabili dalla pagina Download (Wiki Download); inoltre, i file "Logs / cfg" sono disponibili per ogni analisi. Si tenga tuttavia a mente che il sistema di download prepara sempre i risultati dell'analisi più recente con le caratteristiche specificate. Nel caso in cui si desideri investigare l'esecuzione di analisi meno recenti, si può usare la funzione di download tramite RIS_CD.
Non vedo le analisi di altri utenti o le analisi lanciate automaticamente in “Pipeline lanciate”. Non posso accedervi?
Risposta: Le schede delle analisi lanciate da altri utenti non possono essere visualizzate in "Pipeline lanciate": solo gli amministratori possono vedere tutte le analisi lanciate sul sistema. I risultati di quelle analisi sono comunque disponibili per il download, quindi si ha in ogni caso accesso ai risultati, ai report ed ai QC, compresi i dati visualizzati nelle tabelle dei Controlli Qualità.
Nel caso in cui alcuni campioni siano stati analizzati più di una volta con gli stessi software, come faccio a visualizzare solo le informazioni relative ad una determinata esecuzione?
Risposta: Ogni analisi lanciata possiede un codice univoco. In "Risultati Analisi" è possibile filtrare analisi eseguite su campioni con lo stesso NRG ma DS diversi, sfruttando il campo "Cerca" o i filtri nella colonna "Codice". Se si conosce il codice sarà sufficiente eseguire una ricerca per quella stringa di testo, altrimenti è possibile risalirvi in base alla data di esecuzione (ad esempio, cercando o filtrando per "210923" si ottengono le analisi lanciate 23 settembre 2021; analogamente si può specificare un'ora: "240208152038" sta per l'8 febbraio 2024 alle 15.20 e 38 secondi).
È possibile vedere con che programmi/opzioni sono state svolte le analisi?
Risposta: Certamente. Nella cartella di ogni analisi sono conservati i log ed un file ".cfg", il quale corrisponde allo script Bash eseguito per lanciare il tool, con tutti i parametri indicati. Di conseguenza i programmi, le loro versioni, le versioni Docker, i comandi e le opzioni usati per il lancio dell'analisi vengono sempre conservati e sono consultabili in diversi modi:
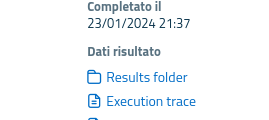
- Per le analisi eseguite ed accessibili nella pagina "Pipeline lanciate", è possibile ottenere informazioni leggendo il file "Execution trace", disponibile nella scheda dell'analisi, sezione "Dati risultato", che contiene la versione dei vari tool eseguiti:
-
Per le analisi importate nel sistema, ovvero presenti in "Risultati analisi", è possibile scaricarne i risultati ed indicare, tra le azioni di download, anche "Logs / cfg". Aprendo la cartella del download dei risultati dell'analisi, nella cartella "logs" sarà presente il file di configurazione, contenente lo script Bash eseguito ed i parametri.
-
I tools (con relative versioni) che concorrono al calcolo dei profili allelici sono anche descritti nella pagina "NGSManagerSOP".
Gestione profilo
Come faccio a cambiare profilo?
Risposta: Si può cambiare il proprio profilo cliccando sul nome del profilo corrente (in alto a destra) e poi su "Cambia gruppo". La procedura è anche illustrata nella videoguida "Profili utente".
Come faccio a cambiare la mia password?
Risposta: Trovi una descrizione delle procedure di cambio password nella pagina Gestione password.
