Pipeline Klebsiella - Kleborate
Introduzione
Lo screening dei genomi di Klebsiella pneumoniae e del complesso di specie di Klebsiella pneumoniae (K. pneumoniae species complex, KpSC) viene effettuato attraverso la pipeline Kleborate.
Kleborate analizza il genoma per ottenere dati riguardo a:
- Specie;
- MLST del complesso di specie di Klebsiella pneumoniae;
- loci di virulenza associati a ICEKp: yersiniabactin (ybt), colibactin (clb), salmochelin (iro), hypermucoidy (rmp);
- loci di virulenza associati a plasmidi: salmochelin (iro), aerobactin (iuc), hypermucoidy (rmp, rmpA2);
- determinanti di resistenza antimicrobica (AMR): geni acquisiti, SNPs, geni troncati e β-lattamasi intrinseche, antigeni K (capsule) e O (LPS);
- sierotipo, tramite alleli wzi e il software Kaptive.
Pagina GitHub di Kleborate: https://github.com/klebgenomics/Kleborate
Lancia pipeline Kleborate
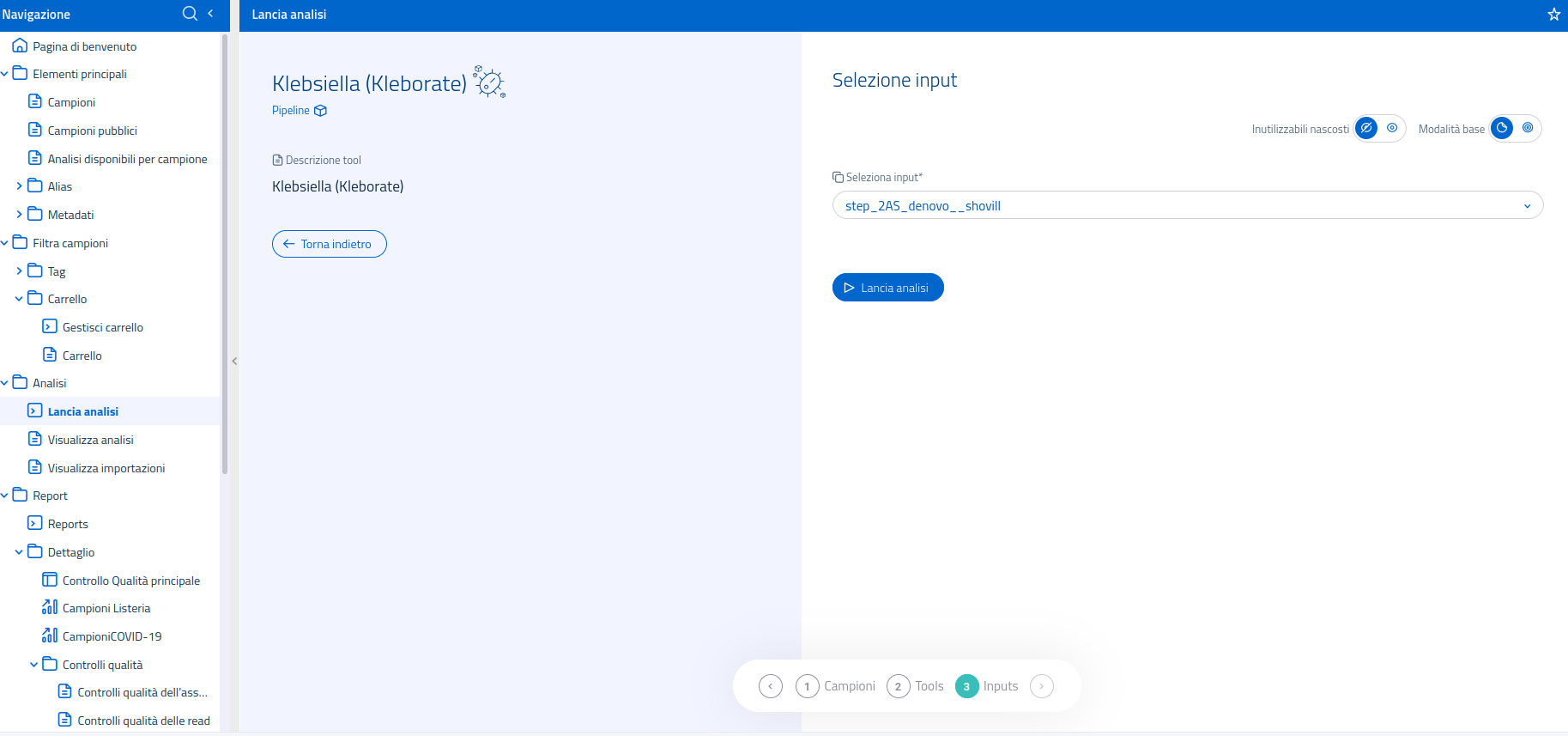
Nel sistema di lancio di analisi, è possibile usare il filtro in alto per visualizzare esclusivamente le pipelines. Una volta selezionata la pipeline Klebsiella (Kleborate), sarà possibile lanciare l'analisi, usando come input l'assemblaggio de novo:
L'interfaccia per la selezione dell'input mette inoltre a disposizione la modalità di selezione input avanzata, per permettere l'utilizzo di input processati da metodi diversi, usati a monte nel flusso di analisi.
Una volta lanciata la pipeline, la pagina genererà un link alla sezione Controllo analisi, per permettere di visualizzare lo stato del processo. L'utente verrà notificato dal sistema sia una volta lanciata con successo la pipeline, sia al termine dell'esecuzione.
Risultati
La pipeline "Kleborate" produce un unico output: una tabella .tsv con tutti i dati di tipizzazione elaborati dal software.
| File | Descrizione | Posizione |
|---|---|---|
*_kleborate.tsv |
tabella .tsv contenente tutti i risultati della tipizzazione | cartella "result" |
