Pipeline Typing on Bacteria
Introduzione
La pipeline Typing on Bacteria esegue, in un unico lancio, tutte le analisi di tipizzazione a cui vengono solitamente sottoposti i campioni di batteri, includendo:
- calcolo della specie;
- identificazione di geni associati ad antibiotico-resistenza e virulenza;
- identificazione della variante del locus flaA (Campylobacter);
- MLST;
- MLST del core-genome;
- MLST del genoma completo;
- annotazione del genoma;
- calcolo della copertura orizzontale e verticale.
La pipeline Typing on Bacteria esegue le seguenti analisi:
- 3TX_species: calcolo della specie con kmerfinder, per assegnare il best reference da usare per il mapping a valle. Quando eseguito da NGSmanager, gli input sono gli scaffolds del de novo da Shovill (pipeline WGS on Bacteria);
- 4AN_AMR: identificazione di geni correlati ad antibiotico-resistenza e virulenza;
- 4TY_flaA: determinazione della variante del locus flaA (solo per Campylobacter);
- 4TY_MLST: Multi-Locus Sequence Typing in silico con software MLST;
- 4TY_cgMLST: MLST del core-genome con software ChewBBACA;
- 4TY_wgMLST: MLST del genoma completo con software ChewBBACA;
- 4TY_serotype: identificazione del sierotipo;
- 4AN_genes: annotazione funzionale del genoma con Prokka;
- Kleborate su campioni di Klebsiella.
Sulla base dei risultati di kmerfinder (3TX_species) vengono inoltre eseguite:
- 4TY_cgMLST;
- 2AS_mapping con Bowtie: il reference usato è quello identificato come best reference da kmerfinder, tra i genomi presenti nel database statico disponibile (kmerfinder).
Il software eseguito, per le analisi 4TY_cgMLST e 4TY_wgMLST, viene selezionato in base agli schemi disponibili per ciascun tool, come indicato nelle pagine Wiki dedicate:
Analogamente: - 4TY_MLST_mlst viene eseguito solo se è disponibile lo schema per il microrganismo (la lista di schemi è consultabile nella guida ufficiale di mlst su GitHub); - 4TY_flaA viene eseguito solo su campioni di Campylobacter; - 4TY_cgMLST_mentalist, su reads trimmate, viene eseguito solo in caso di campioni di Listeria monocytogenes.
Lancia la pipeline Typing on Bacteria
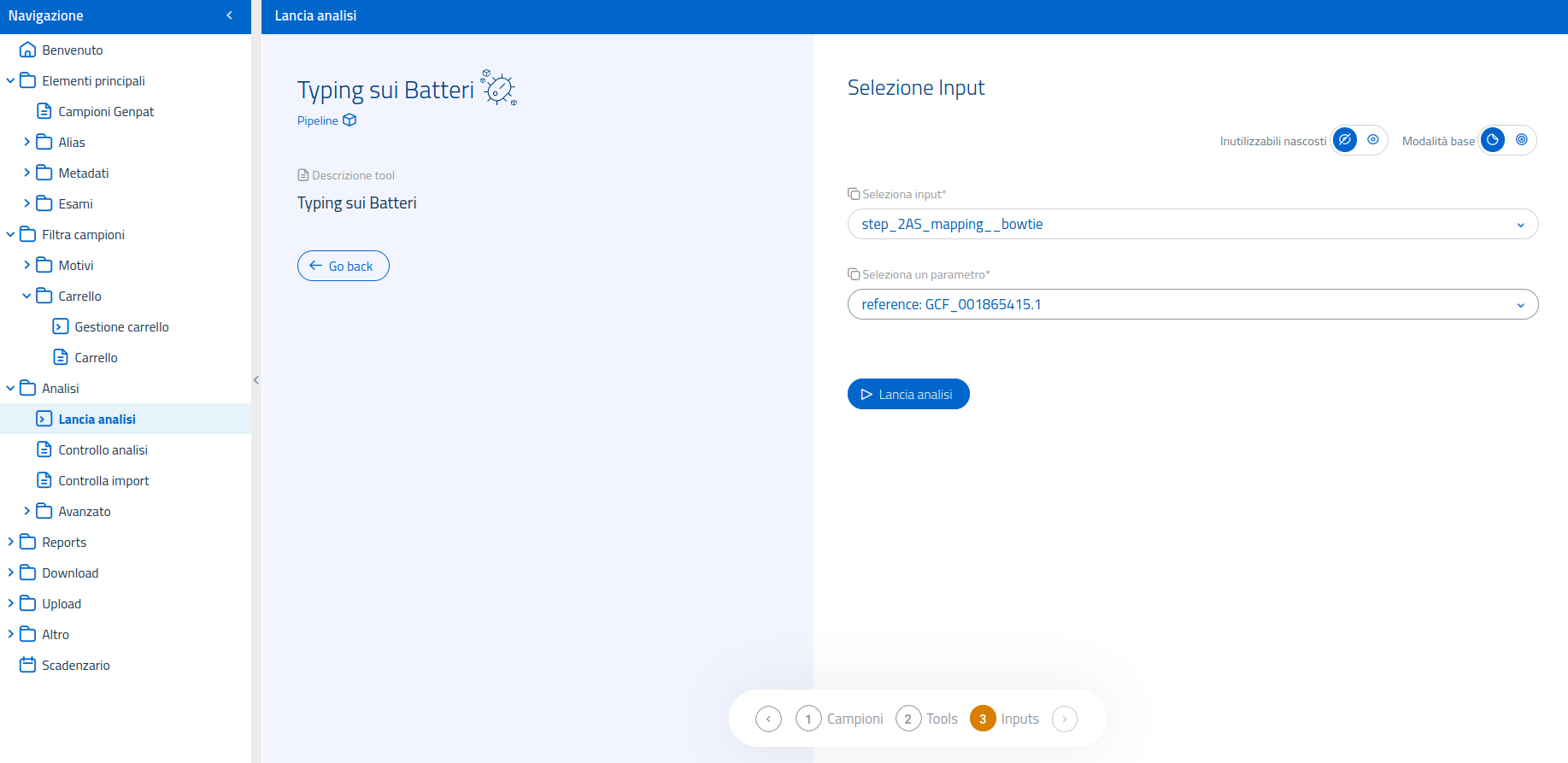
Nel sistema di lancio analisi, è possibile usare il filtro in alto per visualizzare esclusivamente le pipelines. Una volta selezionata la pipeline Typing su Batteri nella pagina dedicata al lancio di analisi, il sistema passerà ad un'interfaccia di conferma.
Gli input utilizzabili sono le sequenze consensus (formato .fasta) prodotte dal mapping (2AS_mapping) o gli scaffolds del de novo assembly (2AS_denovo).
Nel caso vengano usate, come input, le sequenze consensus del mapping, sarà anche necessario specificare un genoma reference tra quelli disponibili.
L'interfaccia per la selezione dell'input mette inoltre a disposizione la modalità di selezione input avanzata, per permettere l'utilizzo di input processati da metodi diversi, usati a monte nel flusso di analisi.
Una volta lanciata la pipeline, la pagina genererà un link alla sezione Controllo analisi, per permettere di visualizzare lo stato del processo. L'utente verrà notificato dal sistema sia una volta lanciata con successo la pipeline, sia al termine dell'esecuzione.
Risultati
I files prodotti dalla pipeline Typing on Bacteria saranno gli stessi prodotti dalle analisi che la compongono, organizzati secondo la stessa gerarchia. Come riferimento, si rimanda quindi alle relative sezioni delle singole analisi:
- Output dell'assegnazione della specie;
- Output della predizione di antibiotico-resistenza e virulenza;
- Output per la determinazione della variante del locus flaA;
- Output del Multi-Locus Sequence Typing (MLST);
- Output di MLST del core-genome (cgMLST);
- Output di MLST del genoma completo (wgMLST);
- Output dell'annotazione del genoma;
- Output del mapping sui risultati di kmerfinder.
