1PP_hostdepl
Introduzione
L'analisi 1PP_hostdepl mappa le read contro il genoma dell'organismo ospite selezionato, permettendo di rimuovere le read contaminanti dell'ospite dai file FASTQ (deplezione delle sequenze dell'ospite).
I file di output sono dei nuovi file FASTQ di read ripulite.
Lancia analisi 1PP_hostdepl
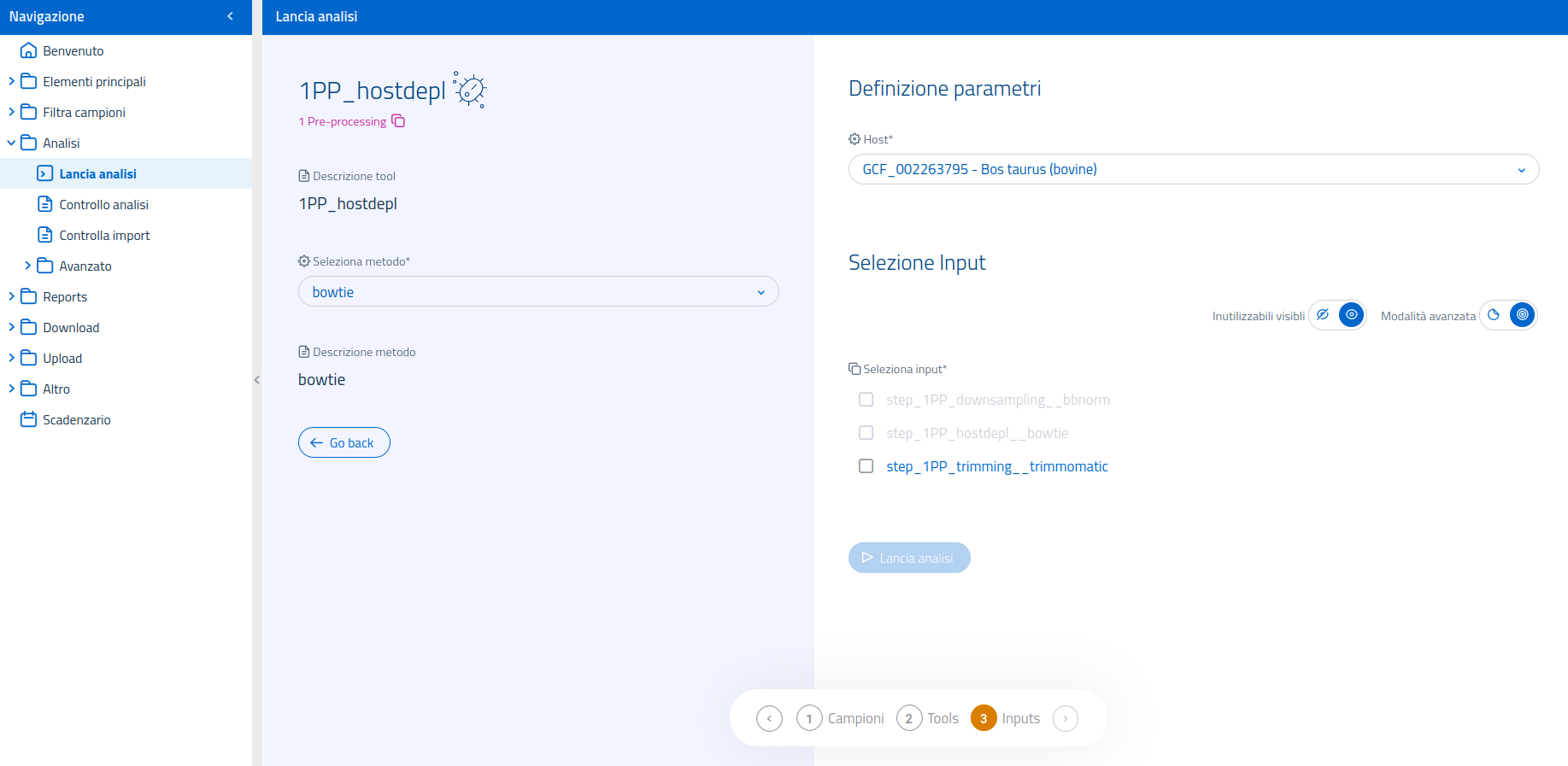
Una volta selezionata l'analisi 1PP_hostdepl nella pagina dedicata al lancio di analisi, sarà possibile selezionare il software bioinformatico ("metodo") da usare tra quelli disponibili per l'analisi. I tool utilizzabili per questa analisi sono:
-
Per tutte le read:
-
Bowtie - un allineatore di short reads ultrarapido ed efficiente in termini di memoria.
Pagina GitHub di Bowtie: https://github.com/BenLangmead/bowtie
-
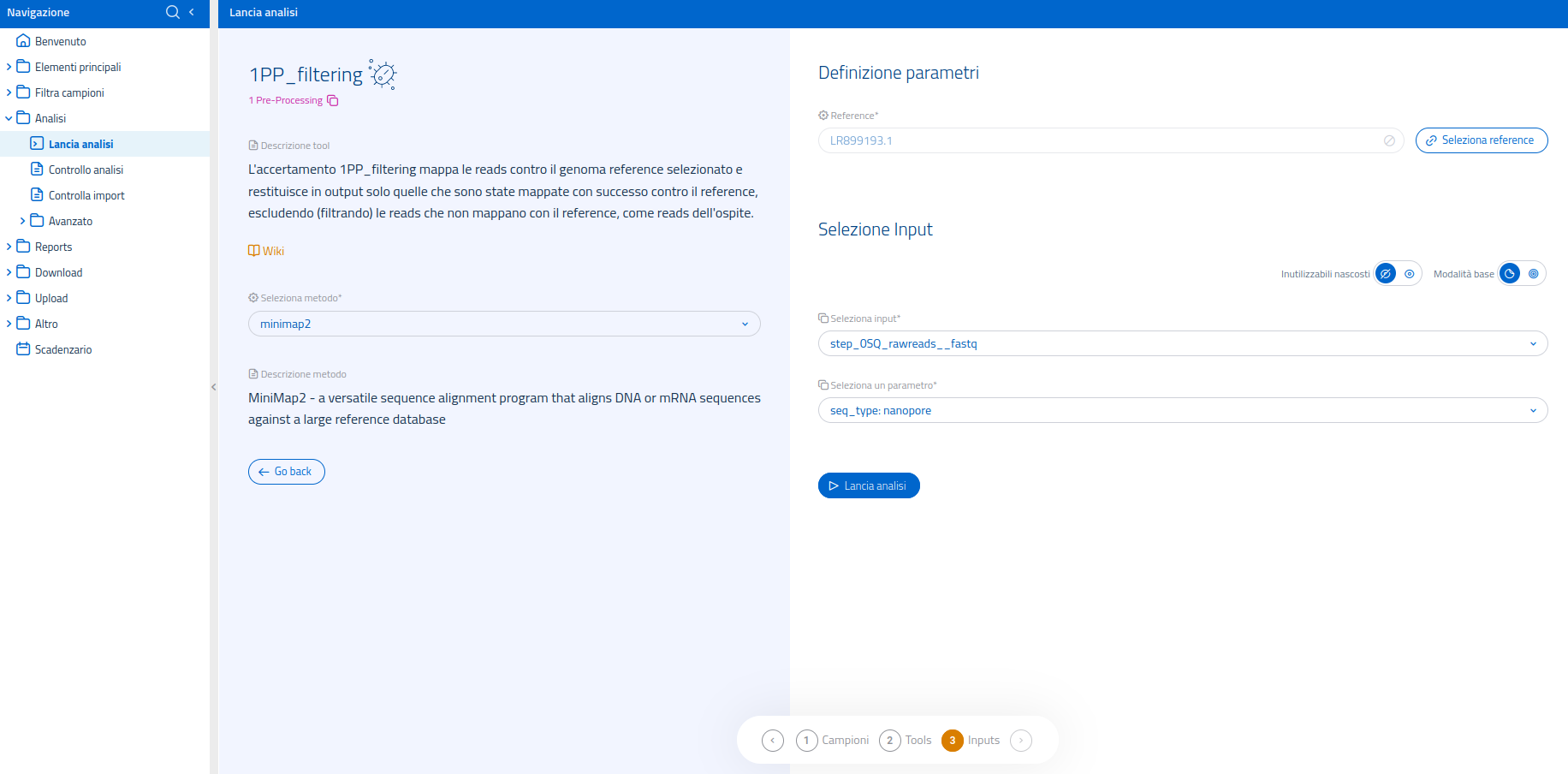
Solo per long reads da apparati con tecnologia nanopore:
-
minimap2 - un programma versatile di allineamento che allinea sequenze di DNA o mRNA contro un ampio database di riferimento.
Pagina GitHub di minimap2: https://github.com/lh3/minimap2
Nella sezione dedicata alla selezione dell'input, sarà necessario indicare sia le read di input che un reference, come parametro addizionale. La deplezione dell'ospite avviene, infatti, mappando le read dei file FASTQ contro un genoma di riferimento, quello dell'ospite, le cui sequenze contaminanti devono essere riconosciute ed eliminate dalle read. Nella definizione del parametro Host, sarà pertanto possibile selezionare uno qualunque dei genomi di riferimento per specie caricate in GenPat.
Nota: Nel caso in cui l'ospite desiderato non sia presente tra quelli disponibili, si invita ad inoltrare una richiesta tramite e-mail al reparto bioinformatica (bioinformatica@izs.it), per l'aggiunta del genoma di riferimento in GenPat.
La schermata di selezione input di questa analisi mette a disposizione dell'utente la modalità di selezione input avanzata, in modo da poter selezionare contemporaneamente file FASTQ precedentemente processati in modo diverso.
Input per Bowtie:
- step_1PP_trimming
- step_1PP_hostdepl
- step_1PP_downsampling
Input per minimap2:
- step_0SQ_rawreads
Se il software selezionato è minimap2, gli input potranno provenire eclusivamente da step_0SQ_rawreads di single long reads prodotte da dispositivi basati su tecnologia nanopore. Per ulteriori informazioni sul software minimap2, si invita a consultare la pagina GitHub ufficiale di minimap2.
Una volta lanciata l'analisi, la pagina genererà un link alla sezione Controllo analisi, per permettere di visualizzare lo stato del processo. L'utente verrà notificato dal sistema sia una volta lanciata con successo l'analisi, sia al termine dell'esecuzione.
Cartella dei risultati
Per consultare la guida sul download dei files dalla piattaforma si faccia riferimento all'apposita pagina.
La cartella dei risultati, Result folder, è accessibile cliccando sul link presente all'interno della scheda dell'analisi, nella sezione Dati risultato. All'interno della conseguente cartella results, è possibile trovare 2 sotto-cartelle:
- meta: (metadati) in cui vengono salvati i file di log e di configurazione del processo eseguito.
- result: in cui sono salvati i file con i risultati prodotti dall'analisi.
Le tabelle sottostanti presentano la lista di files prodotti dai tool disponibili per 1PP_hostdepl, insieme ad alcune informazioni utili.
Bowtie:
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_R1_vdhost_HOSTID.fastq | read 1 (R1) depleta | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_R2_vdhost_HOSTID.fastq | read 2 (R2) depleta | cartella "result" |
minimap2:
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXX-DTXXXXXX_ID_minimap2_HOSTID.fastq.gz | fastq depleto della single read da nanopore device (file compresso) | cartella "result" |
