MAFFT
Introduzione
L'analisi MAFFT esegue il multiallineamento di sequenze; l'analisi è seguita dal lancio di ReporTree come analisi di clustering.
MAFFT produce il file FASTA del multiallineamento utilizzato come input di ReporTree. Quest'ultimo invece produce la matrice di distanza e l'albero "Minimum Spanning Tree" (MSTree o MST). Opzionalmente; l'analisi può anche calcolare il grafico del "clustering gerarchico" (Hierarchical Clustering, HC).
- Sito ufficiale di MAFFT: https://mafft.cbrc.jp/alignment/software/
- Pagina GitHub di MAFFT: https://github.com/GSLBiotech/mafft
- Pagina GitHub di ReporTree: https://github.com/insapathogenomics/ReporTree
- Pagina GitHub di IQ-TREE: https://github.com/iqtree/iqtree2
- Pagina GitHub di FastTree: https://github.com/morgannprice/fasttree
Una volta calcolato l'albero MST, è possibile visualizzarlo direttamente in piattaforma usando il sistema integrato di visualizzazione degli alberi (SPREAD), accessibile dalla scheda dell'analisi completata.
Lancia l'analisi MAFFT
Una volta selezionata l'analisi MAFFT nella pagina dedicata al lancio di analisi, il sistema passerà ad un'interfaccia di conferma, mettendo anche a disposizone la modalità di selezione input avanzata. Tale funzionalità permette l'utilizzo di input prodotti da software diversi, a monte del flusso di analisi.
L'analisi produce il file di multiallineamento successivamente utilizzato da ReporTree. I file di input per la costruzione del multifasta sono quindi i singoli file FASTA dei campioni, i quali possono essere forniti come:
- step_2AS_mapping
- step_2AS_denovo
- step_2AS_hybrid
- step_2AS_import
La schermata di definizione dei parametri offre un elevato livello di personalizzazione, tra cui:
- Parametri di MAFFT:
Custom parameters for MAFFT: campo di testo per le opzioni in stile Command Line, in cui specificare i modificatori da passare a MAFFT;
-
Parametri di ReporTree:
Partition threshold for clustering definition: permette di personalizzare i valori soglia per la creazione delle partizioni dell'albero;Minimum proportion of samples per site without missing data: ReporTree normalmente considera, per il calcolo della matrice di distanza e dell'albero, tutti i siti dei genomi allineati. Questa opzione permette di definire un valore soglia: i siti che presentano una percentuali di "missing data", ovvero una percentuale di N (%N) al di sotto del valore specificato, vengono scartati. Solo i siti che passano il filtro vengono conservati ed usati per il calcolo dell'albero;Minimum proportion (0 to 1) of ATCG in informative sites of the alignment per sample: ReporTree normalmente utilizza tutti i campioni forniti per il calcolo della matrice di distanza e dell'albero. Questa opzione consente di definire un valore soglia per la percentuale di N nella sequenza del campione. I campioni con %N al di sotto del valore specificato vengono scartati;- Opzioni
Sample of interest: consentono di specificare uno o più campioni di interesse su cui ReporTree ricalcola uno "Zoom", ovvero un albero contenente solo il campione (o i campioni) d'interesse e i campioni appartenenti allo stesso cluster; - Opzioni
Method used in HC clustering to create a dendrogram: selezione della modalità opzionale per lo Hierarchical Clustering; - Opzioni
Custom parameters for reportree: campi di testo in cui immettere opzioni in stile Command Line, da passare a ReporTree esclusivamente per il calcolo degli alberi specificati nell'opzione (MST prodotto con Grapetree o HC);
-
Parametri per clustering ML:
Maximum likelood phylogenetic tree calculation: permette di scegliere il software da utilizzare per il clustering opzionale con algoritmo ML. I sofware disponibili sono IQ-TREE e FastTree;Custom parameters for ML phylogenetic tree calculation: campo di testo in cui immettere opzioni in stile Command Line per il clustering ML;[IQ-TREE only] Try to apply CMAPLE tree search algorithm: se viene selezionato IQ-TREE, permette di scegliere se applicare l'algoritmo per il posizionamento nell'albero di CMAPLE, integrato in IQ-TREE.
Dato il numero e la complessità dei parametri di ReporTree, si invita a consultare la guida ufficiale di ReporTree per maggiori informazioni sull'utilizzo del software.
La procedura per il lancio dell'analisi è analoga ad altre analisi che comprendono l'esecuzione di ReporTree:
Una volta lanciata l'analisi, la pagina genererà un link alla sezione Controllo analisi, per permettere di verificare lo stato del processo. L'utente verrà notificato dal sistema sia una volta lanciata con successo l'analisi, sia al termine dell'esecuzione.
Nella scheda dell'analisi completata saranno presenti alcune opzioni, oltre alla possibilità di esplorare la cartella dei risultati, come l'accesso diretto ad alcuni dei file di log e metadati, l'apertura del file nwk e la visualizzazione diretta dell'albero MSTree tramite l'integrazione di SPREAD in piattaforma.
Per visualizzare l'albero sarà necessario navigare nella scheda del risultato di GrapeTree e selezionare il link Minimum Spanning Tree with SPREAD:
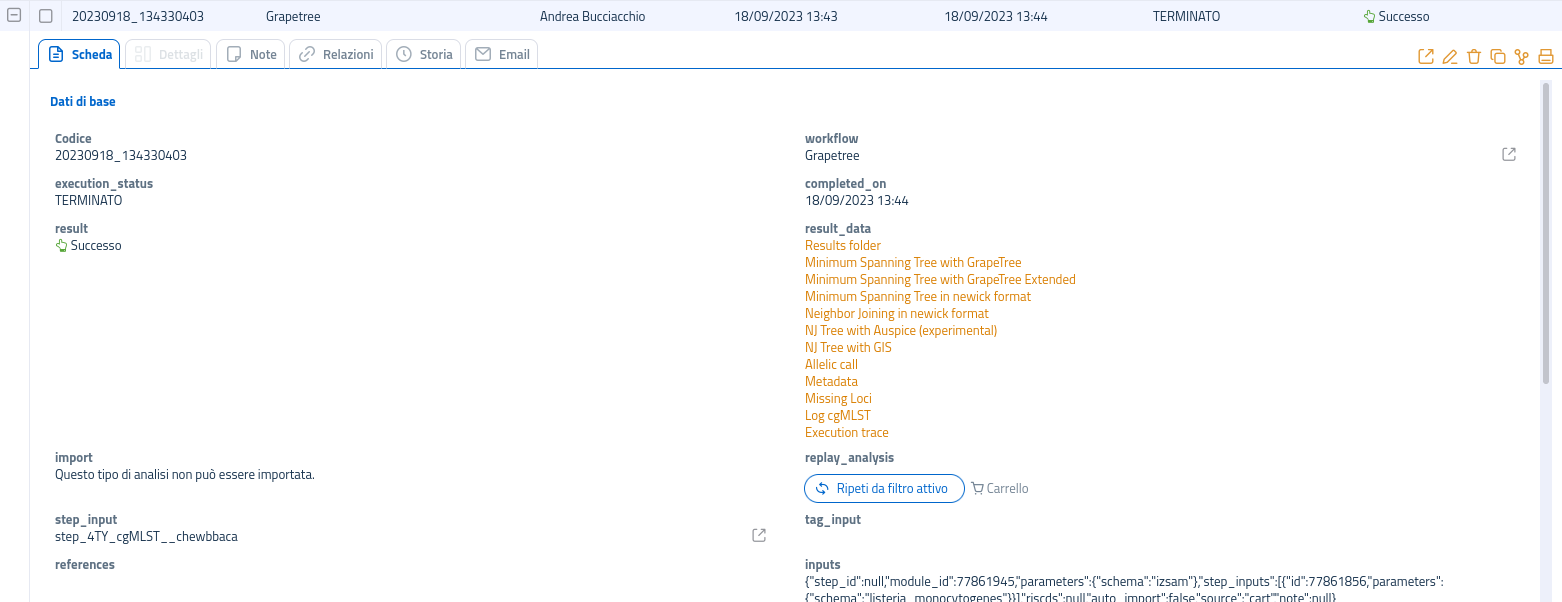
Nota: I risultati delle analisi multi-campione non possono essere importati. Si invita a sfruttare l'apposita funzionalità per la conservazione delle analisi non importabili o, in alternativa, l'opzione per il download diretto del file newick (
.nwk) e del file dei metadati, in modo da poter conservare i file e visualizzare l'albero in qualunque momento, sia all'interno della piattaforma che con un software esterno.
Cartella dei risultati
Per consultare la guida sul download dei file dalla piattaforma si faccia riferimento all'apposita pagina.
La cartella dei risultati, Result folder, è accessibile cliccando sul link presente all'interno della scheda dell'analisi, nella sezione Dati risultato. All'interno della conseguente cartella results è possibile trovare 2 sotto-cartelle:
- meta: ("metadata") in cui vengono salvati i file di log e di configurazione del processo eseguito.
- result: in cui sono salvati i file con i risultati prodotti dall'analisi.
La tabella in basso presenta la lista dei principali file di interesse presenti nelle cartelle, insieme ad alcune informazioni utili.
| File | Descrizione | Posizione |
|---|---|---|
gt.nwk |
file .nwk dell'albero MST | cartella "result" |
gt_dist_grapetree.tsv |
matrice di distanza per l'albero MST | cartella "result" |
alignment.fasta |
multifasta dell'allineamento dei campioni | cartella "result" |
reportree_metadata.tsv |
tabella dei metadati dei campioni prodotta da ReporTree | cartella "result" |
gt_dist.tsv |
distanze pairwise dell'albero MST | cartella "result" |
gt_clusterComposition.tsv |
Tabella con elenco dei cluster e loro composizione | cartella "result" |
gt_loci_used.txt |
elenco dei loci usati per il calcolo della matrice di distanza (start position) | cartella "result" |
multifasta.fasta |
multifasta delle sequenze non ancora allineate dei campioni | cartella "result" |
gt_dist_hamming.tsv |
matrice di distanza | cartella "result" |
gt_partitions.tsv |
tabella con le informazioni dei cluster di appartenenza dei campioni, ad ogni valore di partizionamento dell'albero | cartella "result" |
zooms.txt |
elenco degli zoom richiesti | cartella "result" |
gt_metadata_w_partitions.tsv |
Tabella dei metadati con informazioni sui cluster di appartenenza | cartella "result" |
gt_partitions_summary.tsv |
tabella riepilogativa delle partizioni dell'albero e relativi campioni nei cluster | cartella "result" |
Il file in formato newick (.nwk) contiene tutti i dati dell'albero e può essere visualizzato tramite SPREAD o un altro software esterno per la visualizzazione di dendrogrammi o grafici di distanza.
