4AN_AMR
Introduzione
L'analisi 4AN_AMR (Anti-Microbial Resistance) predice la presenza di geni correlati ad antibiotico-resistenza e di geni di virulenza, nella sequenza ricostruita del microrganismo di interesse.
Lancia analisi 4AN_AMR
Una volta selezionata l'analisi 4AN_AMR nella pagina dedicata al lancio di analisi, sarà possibile selezionare il software bioinformatico ("metodo") da usare tra quelli disponibili. I metodi utilizzabili per questa analisi sono:
Per tutti i microrganismi:
-
ABRicate - Screening massivo dei contig per geni di virulenza o di resistenza agli antibiotici
Pagina GitHub di ABRicate: https://github.com/tseemann/abricate
-
AMRFinderPlus - AMRFinderPlus identifica geni di resistenza antimicrobica, acquisiti in sequenze proteiche batteriche e/o in sequenze nucleotidiche assemblate, nonché mutazioni puntiformi note, associate alla resistenza, per diversi taxa.
Pagina GitHub di AMRFinderPlus: https://github.com/ncbi/amr/wiki/Running-AMRFinderPlus#usage
-
ResFinder - identificazione dei geni di resistenza antimicrobica acquisiti.
Pagina GitHub di ResFinder: https://github.com/cadms/resfinder
-
PlasmidFinder - identificazione di geni per l'identificazione e la tipizzazione di plasmidi.
Pagina GitHub di PlasmidFinder: https://github.com/genomicepidemiology/plasmidfinder
Per Klebsiella pneumoniae (ma anche per K. oxytoca e Escherichia genus):
- Kleborate - un tool per effettuare lo screening sugli assemblaggi genomici di Klebsiella pneumoniae e del suo complesso di specie (KpSC).
Pagina GitHub di Kleborate: https://kleborate.readthedocs.io/en/latest/Usage.html
Solo per Escherichia coli:
- patho_typing - identificazione dei geni di resistenza antimicrobica acquisiti.
Pagina GitHub di patho_typing: https://github.com/B-UMMI/patho_typing
Solo per Staphylococcus aureus:
- BLAST - il Basic Local Alignment Search Tool identifica regioni di similarità tra sequenze biologiche.
Pagina GitHub di BLAST: https://github.com/ncbi/blast_plus_docs
Solo per Campylobacter:
- staramr - (*AMR) compila un report di sintesi dei geni di resistenza antimicrobica rilevati.
Pagina GitHub di staramr: https://github.com/phac-nml/staramr
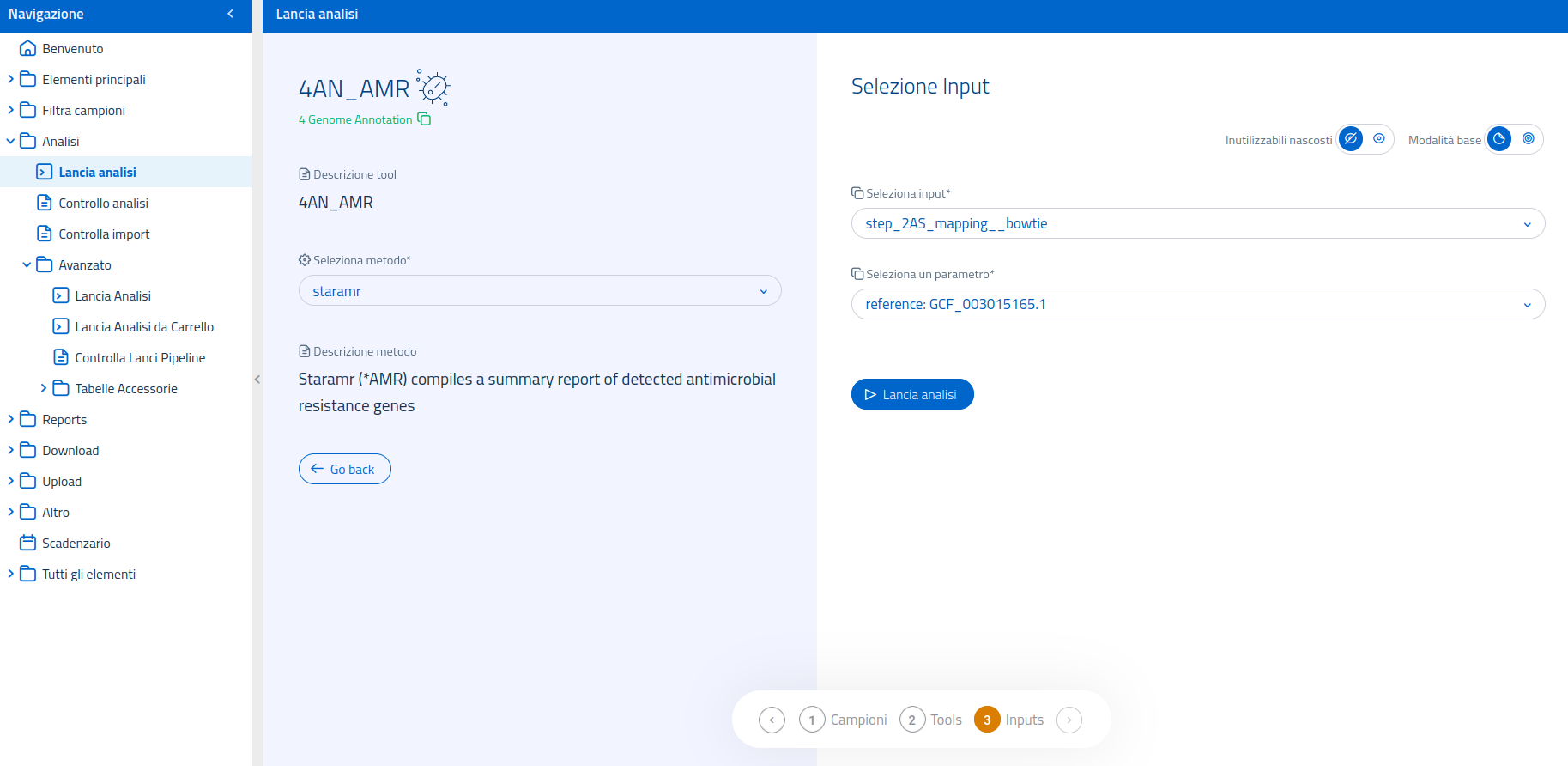
Per 4AN_AMR è necessario specificare le sequenze di input - provenienti da un assembly de novo o da un mapping - e indicare il genoma reference utilizzato per il mapping, se quest'ultimo viene selezionato come input.
L'interfaccia per la selezione dell'input mette inoltre a disposizione la modalità di selezione input avanzata, per permettere l'utilizzo di input processati da metodi diversi, usati a monte nel flusso di analisi.
I possibili input possono provenire da:
- step_2AS_mapping
- step_2AS_denovo
- step_2MG_denovo
- step_2AS_import
Nota: in aggiunta ai tool per l'indagine di Resistenza Antimicrobica (AMR), tra i software disponibili è elencato anche "Filtering" che non esegue l'AMR: esso filtra i risultati dell'AMR, (eseguita con uno degli altri programmi disponibili), in base ai parametri di coverage e di identità specificati. Gli input utilizzabili sono step_3TX_species__vdabricate e step_4AN_AMR__abricate.
Una volta lanciata l'analisi, la pagina genererà un link alla sezione Controllo analisi, per permettere di visualizzare lo stato del processo. L'utente verrà notificato dal sistema sia una volta lanciata con successo l'analisi, sia al termine dell'esecuzione.
Cartella dei risultati
Per consultare la guida sul download dei file dalla piattaforma si faccia riferimento all'apposita pagina.
La cartella dei risultati, Result folder, è accessibile cliccando sul link presente all'interno della scheda dell'analisi, nella sezione Dati risultato. All'interno della conseguente cartella results, è possibile trovare 2 sotto-cartelle:
- meta: (metadati) in cui vengono salvati i file di log e di configurazione del processo eseguito;
- result: in cui sono salvati i files con i risultati prodotti dall'analisi.
Le tabelle in basso presentano la lista di file presenti nelle cartelle, insieme ad alcune informazioni utili.
ABRicate
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_abricate_calls.txt | file con i risultati dell'allineamento dei geni, coverage e query del database | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_abricate.summary | file di sintesi di ABRicate con geni e relativi coverage | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_output_abricate_AMR.csv | file di sintesi dei geni di antibiotico-resistenze | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_output_abricate_VF.csv | file di sintesi dei geni di virulenza | cartella "result" |
Per ulteriori dettagli riguardo i file prodotti da ABRicate, si invita a consultare il manuale di ABRicate.
BLAST
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_blast_out.tsv | tabella .tsv dei risultati di BLAST | cartella "result" |
staramr
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_staramr_detailed_summary.tsv | tabella .tsv dei risultati organizzati per tipo di dato (gene di resistenza/plasmide/schema MLST...) | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_staramr_mlst.tsv | risultati dello schema MLST a 7-loci per i geni specie-specifici + Sequence Type (ST) | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_staramr_plasmidfinder.tsv | risultati .tsv con le sequenze appartenenti a plasmidi identificati | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_staramr_pointfinder.tsv | risultati dell'AMR in formato .tsv con posizione Pointfinder | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_staramr_resfinder.tsv | risultati della predizione di resistenze e dell'allineamento dei geni di resistenza | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_staramr_results.xlsx | risultati dell'AMR in formato foglio di calcolo | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_staramr_summary.tsv | risultati dell'AMR in formato .tsv | cartella "result" |
ResFinder
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_resfinder_ResFinder_Hit_in_genome_seq.fsa | file fasta con la sequenza del/i gene/i di resistenza identificati nel genoma del campione con header esteso | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_resfinder_ResFinder_Resistance_gene_seq.fsa | file fasta con la sequenza del/i gene/i di resistenza identificati nel genoma del campione con header ridotto | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_resfinder_ResFinder_results.txt | file di testo con tabella riassuntiva ed identità di sequenza | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_resfinder_ResFinder_results_tab.txt | file .tsv con l'elenco dei geni di resistenza identificati (elenca solo i geni presenti) | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_resfinder_ResFinder_results_table.txt | file di testo con l'elenco dei geni di resistenza (specifica sia i geni presenti che quelli non rinvenuti) | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_resfinder_pheno_table.txt | file di testo con i risultati e tabella dei fenotipi | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_resfinder_std_format_under_development.json | cartella "result" |
AMRFinderPlus
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_amrfinderplus.tsv | tabella .tsv con le informazioni sui geni di resistenza identificati | cartella "result" |
kleborate
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_kleborate.tsv | tabella .tsv contenente tutti i risultati della tipizzazione | cartella "result" |
Patho_typing
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_patho_typing_rematchModule_report.txt | tabella .tsv con le informazioni sui geni identificati da ReMatCh | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_patho_typing_report.txt | tabella .tsv con i possibili patotipi identificati | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_patho_typing_extended_report.txt | tabella .tsv con le informazioni sui geni identificati per l'attribuzione del patotipo | cartella "result" |
plasmidfinder
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_plasmidfinder_results.tsv | tabella .tsv con le informazioni sui plasmidi identificati | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_plasmidfinder_kma_*.res/aln/fsa | risultati prodotti da kma dei plasmidi identificati | cartella "result" |
