3TX_species
Introduzione
3TX_species assegna la specie, batterica o virale, più vicina alle sequenze in esame. Se il tool utilizzato è vdabricate, l'analisi identifica il miglior reference virale da utilizzare per le analisi a valle. Kmerfinder è il tool usato per l'identificazione del "best reference" e determina la specie assegnata.
Lancia analisi 3TX_species
Una volta selezionata l'analisi 3TX_species nella pagina dedicata al lancio di analisi, sarà possibile selezionare il software bioinformatico ("metodo") da usare tra quelli disponibili per l'analisi. I metodi utilizzabili per questa analisi sono:
Per l'assegnazione di specie batteriche:
- KmerFinder - Predizione della specie batterica mediante un algoritmo fast K-mer
Pagina GitHub di KmerFinder: https://github.com/kcri-tz/kmerfinder.
Per l'assegnazione di specie virali:
- vdabricate - Screening massivo dei contig per specie virali di un database predefinito utilizzando Abricate.
Il tool vdabricate può essere utilizzato per l'identificazione del genoma reference migliore per un virus di interesse, in base alle corrispondenze di sequenza trovate nel database delle sequenze virali (DB_Virus).
Per tutte le specie:
-
BLAST - il Basic Local Alignment Search Tool identifica regioni di similarità tra sequenze biologiche.
Pagina GitHub di BLAST: https://github.com/ncbi/blast_plus_docs.
-
Mash - stima rapida della distanza tra genomi e matagenomi mediante MinHash.
Pagina GitHub di Mash: https://github.com/marbl/Mash.
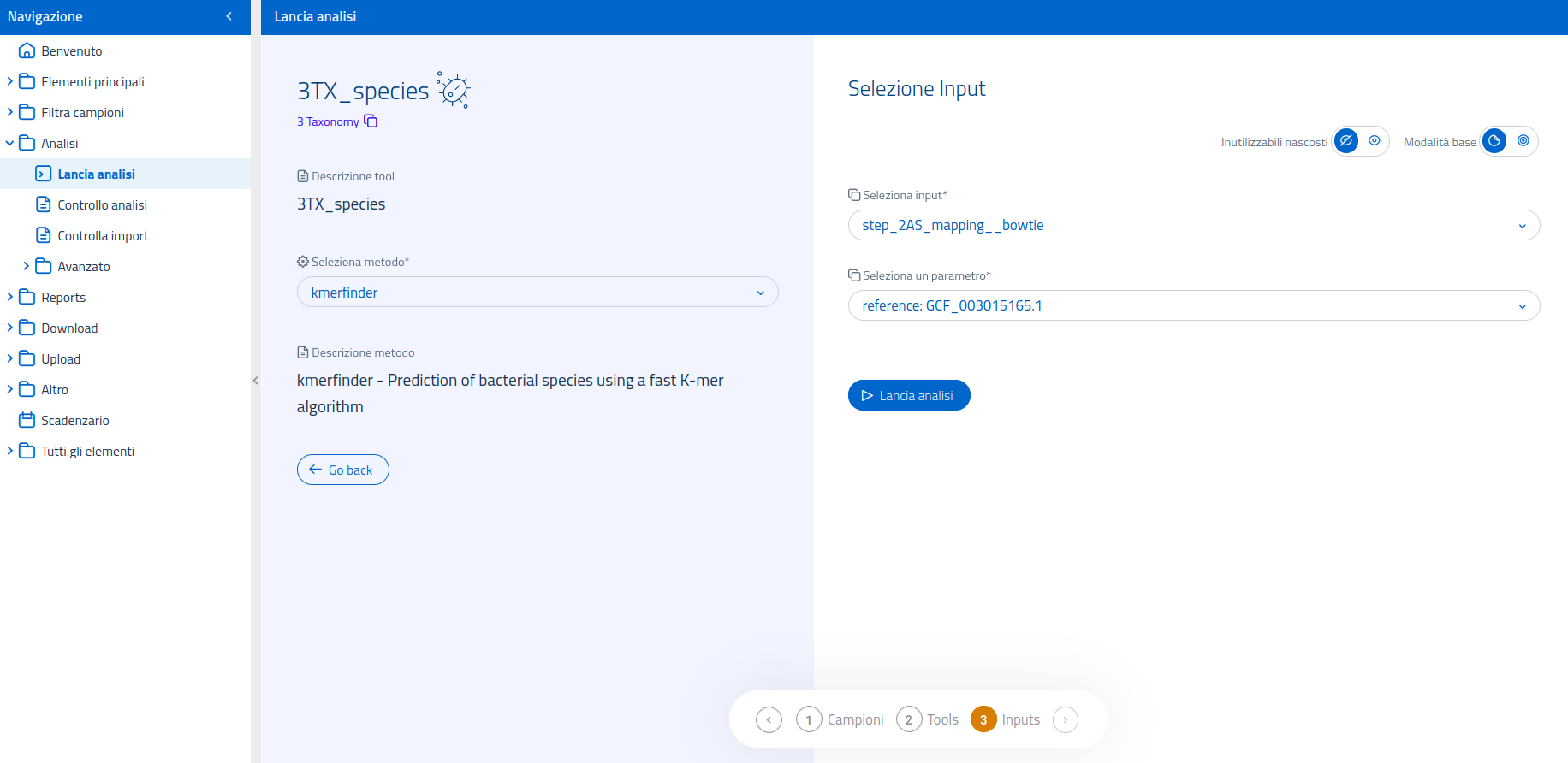
Per 3TX_species è necessario specificare le sequenze di input - provenienti da un assembly de novo o da un mapping - e indicare il genoma reference utilizzato per il mapping, se quest'ultimo viene selezionato come input.
L'interfaccia per la selezione dell'input mette inoltre a disposizione la modalità di selezione input avanzata, per permettere l'utilizzo di input processati da metodi diversi, usati a monte nel flusso di analisi.
I possibili input utilizzabili per 3TX_species sono:
Una volta lanciata l'analisi, la pagina genererà un link alla sezione Controllo analisi, per permettere di visualizzare lo stato del processo. L'utente verrà notificato dal sistema sia una volta lanciata con successo l'analisi, sia al termine dell'esecuzione.
Cartella dei risultati
Per consultare la guida sul download dei files dalla piattaforma si faccia riferimento all'apposita pagina.
La cartella dei risultati, Result folder, è accessibile cliccando sul link presente all'interno della scheda dell'analisi, nella sezione Dati risultato. All'interno della conseguente cartella results, è possibile trovare 2 sotto-cartelle:
- meta: (metadati) in cui vengono salvati i file di log e di configurazione del processo eseguito;
- result: in cui sono salvati i files con i risultati prodotti dall'analisi.
Le tabelle sottostanti elencano i files prodotti dai tool disponibili per 3TX_species.
KmerFinder
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_kmerfinder_bacterial.tsv | file con la specie batterica assegnata | cartella "results" |
| DSXXXXXXXX-DTXXXXXX_ID_kmerfinder_viral.tsv | file con la specie virale assegnata | cartella "results" |
vdabricate
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_vdabricate_calls.txt | corrispondenze individuate nel DB_Virus | cartella "result" |
BLAST
| File | Descrizione | Posizione |
|---|---|---|
| results.csv | tabella riassuntiva dei file dei risultati, con campi separati da ";" | cartella "results" |
| DSXXXXXXXX-DTXXXXXX_ID_blast_nt.asn.gz | dati delle sequenze in formato .asn (Abstract Syntax Notation) compresso | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_blast_nt.csv | tabella .csv dei risultati dell'allineamento di sequenza | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_blast_nt.txt | risultati dell'allineamento delle sequenze nell'output standard di BLASTn | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_blast_nt_max_target_seqs_5.csv | tabella .csv dei risultati dell'allineamento, filtrata per le 5 sequenze più vicine | cartella "result" |
Mash
| File | Descrizione | Posizione |
|---|---|---|
| DS9573634-DT230426121427891_2019.TE.13476.1.1_mash_screen.tsv | tabella intermedia, con le percentuali di identità di sequenza, tra il genoma del campione e le sequenze testate | cartella "result" |
| DS9573634-DT230426121427891_2019.TE.13476.1.1_mash_screening_results.tsv | file .tsv con l'assegnazione finale della specie | cartella "result" |
