3TX_class
Introduzione
L'analisi 3TX_class esegue la classificazione tassonomica degli organismi d'origine delle read e include un controllo delle contaminazioni.
3TX_class__kraken produce, appunto, i risultati relativi alla contaminazione, consultabili in Report > Dettaglio > Controlli qualità/Metriche > Controlli qualità dei Taxa.
Lancia analisi 3TX_class
Una volta selezionata l'analisi 3TX_class nella pagina dedicata al lancio di analisi, sarà possibile selezionare il software bioinformatico ("metodo") da usare tra quelli disponibili. I metodi utilizzabili per questa analisi sono elencati nella lista sottostante.
Per tutti i microrganismi:
- Kraken - sistema Kraken di classificazione tassonomica delle sequenze
- Kraken 2 - seconda versione del sistema Kraken di classificazione tassonomica delle sequenze
Pagina GitHub di Kraken: https://github.com/DerrickWood/kraken
Pagina GitHub di Kraken 2: https://github.com/DerrickWood/kraken2
Solo per le specie appartenenti a Escherichia, Salmonella e Listeria:
- ConFindr - progettato per rilevare contaminazioni batteriche, all'interno della stessa specie, nei dati grezzi generati da Illumina
Pagina GitHub di ConFindr: https://github.com/OLC-Bioinformatics/ConFindr/tree/main
Solo per single long reads provenienti da campioni metagenomici sequenziati con tecnologia Nanopore:
- Centrifuge - classificatore per sequenze metagenomiche
Pagina GitHub di Centrifuge: https://github.com/DaehwanKimLab/centrifuge
Nota: Kraken 2 differisce dalla prima versione. Trattandosi di software paralleli, sono entrambi disponibili nel sistema di lancio analisi. Per informazioni riguardo il fuzionamento e le differenze tra Kraken e Kraken 2 si invita a consultare il loro manuale ufficiale al seguente link: https://github.com/DerrickWood/kraken2/blob/master/docs/MANUAL.markdown.
L'interfaccia per la selezione dell'input mette inoltre a disposizione la modalità di selezione input avanzata, per permettere l'utilizzo di input processati da metodi diversi, usati a monte nel flusso di analisi.
I possibili input utilizzabili per 3TX_class sono:
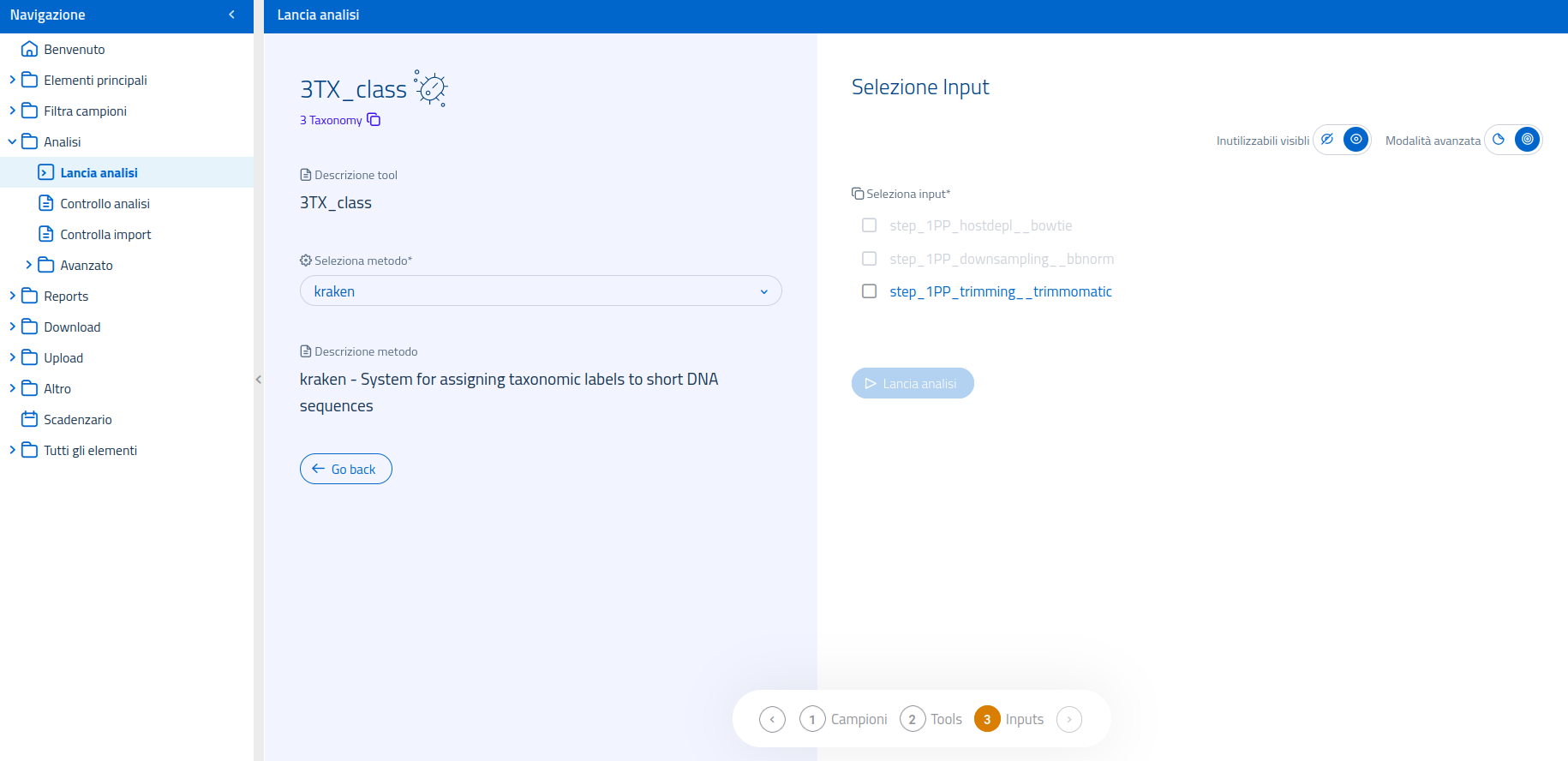
Una volta lanciata l'analisi, la pagina genererà un link alla sezione Controllo analisi, per permettere di visualizzare lo stato del processo. L'utente verrà notificato dal sistema sia una volta lanciata con successo l'analisi, sia al termine dell'esecuzione.
Cartella dei risultati
Per consultare la guida sul download dei files dalla piattaforma si faccia riferimento all'apposita pagina.
La cartella dei risultati, Result folder, è accessibile cliccando sul link presente all'interno della scheda dell'analisi, nella sezione Dati risultato. All'interno della conseguente cartella results, è possibile trovare 2 sotto-cartelle:
- meta: (metadati) in cui vengono salvati i file di log e di configurazione del processo eseguito;
- result: in cui sono salvati i files con i risultati prodotti dall'analisi.
Le tabelle sottostanti elencano i files prodotti dai tool disponibili per 3TX_class. Per maggiori dettagli sui file prodotti dalle due versioni di Kraken, si invita a fare riferimento al manuale di kraken e alla scheda di supporto per Kraken2.
Kraken
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_kraken.tsv | file di classificazione tassonomica di kraken | cartella "result" |
Kraken 2
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_bracken_genus.tsv | abbondanza stimata delle reads a livello di genere di appartenenza rinvenuto | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_bracken_genus_report.tsv | report file di classificazione tassonomica a livello di genere | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_bracken_species.tsv | abbondanza stimata delle reads a livello di specie di appartenenza rinvenuta | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_bracken_species_report.tsv | report file di classificazione tassonomica a livello di specie | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_kraken.tsv | report file di classificazione tassonomica a livello di ceppo | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_kraken.txt.gz | file di testo compresso con le sequenze classificate da kraken 2 | cartella "result" |
ConFindr
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_contamination.csv | tabella .csv delle contaminazioni identificate nel campione da ConFindr | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_rmlst.csv | tabella .csv degli alleli per ogni gene nel campione | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_confindr_report.csv | tabella .csv totale dei campioni e delle contaminazioni identificate da ConFindr | cartella "result" |
Centrifuge
| File | Descrizione | Posizione |
|---|---|---|
| DSXXXXXXXX-DTXXXXXX_ID_centrifuge.output | file di output tabulare di Centrifuge contenente il taxa ID, il relativo score e il secondo miglior score (aprire con editor di testo o fogli di calcolo) | cartella "result" |
| DSXXXXXXXX-DTXXXXXX_ID_centrifuge.report | report tabulare di Centrifuge con la lista degli organismi rinvenuti nel campione e le loro statistiche (aprire con editor di testo o fogli di calcolo) | cartella "result" |
Per ulteriori informazioni sugli output di Centrifuge e sulle caratteristiche del software, si invita a consultare la pagina GitHub ufficiale di Centrifuge.
