Topics
- Home
- Campioni ufficiali
- Elementi principali
- Filtra campioni
-
Analisi
- Lancia analisi
- Fasi e modalità di lancio
- Visualizza analisi
-
Descrizione tools
- Introduzione
- Tools per tecnologie non-Illumina
- Single sample
- Multi sample
-
Pipelines
- Mapping Virus Segmentati
- Covid Emergency
- Deplezione e de novo
- Draft del Genoma
- Enterotoxin S. aureus finder
- LSDV Complete
- Mapping Brucella
- Module AMR
- Nf-core ampliseq
- NgsManager
- Obitools
- Plasmids (AMR)
- Processamento Raw Reads
- Typing su Batteri
- WNV - Lineage Calculation and Mapping
- Filtering & de novo
- Plasmids AMR
- nf-core ampliseq
- Klebsiella (Kleborate)
- Modulo AMR
- QC fastqc
- QC Quast
- QC Nanoplot
- IAEA
- Report
- Download
- Upload
- Gestione Varianti
- Dashboards
- SOP
- Integrazioni SILAB
- Novità
- Supporto
Controlli qualità del cgMLST
La tabella dei Controlli qualità del cgMLST fornisce informazioni sulla qualità del core genome Multi Locus Sequence Typing.
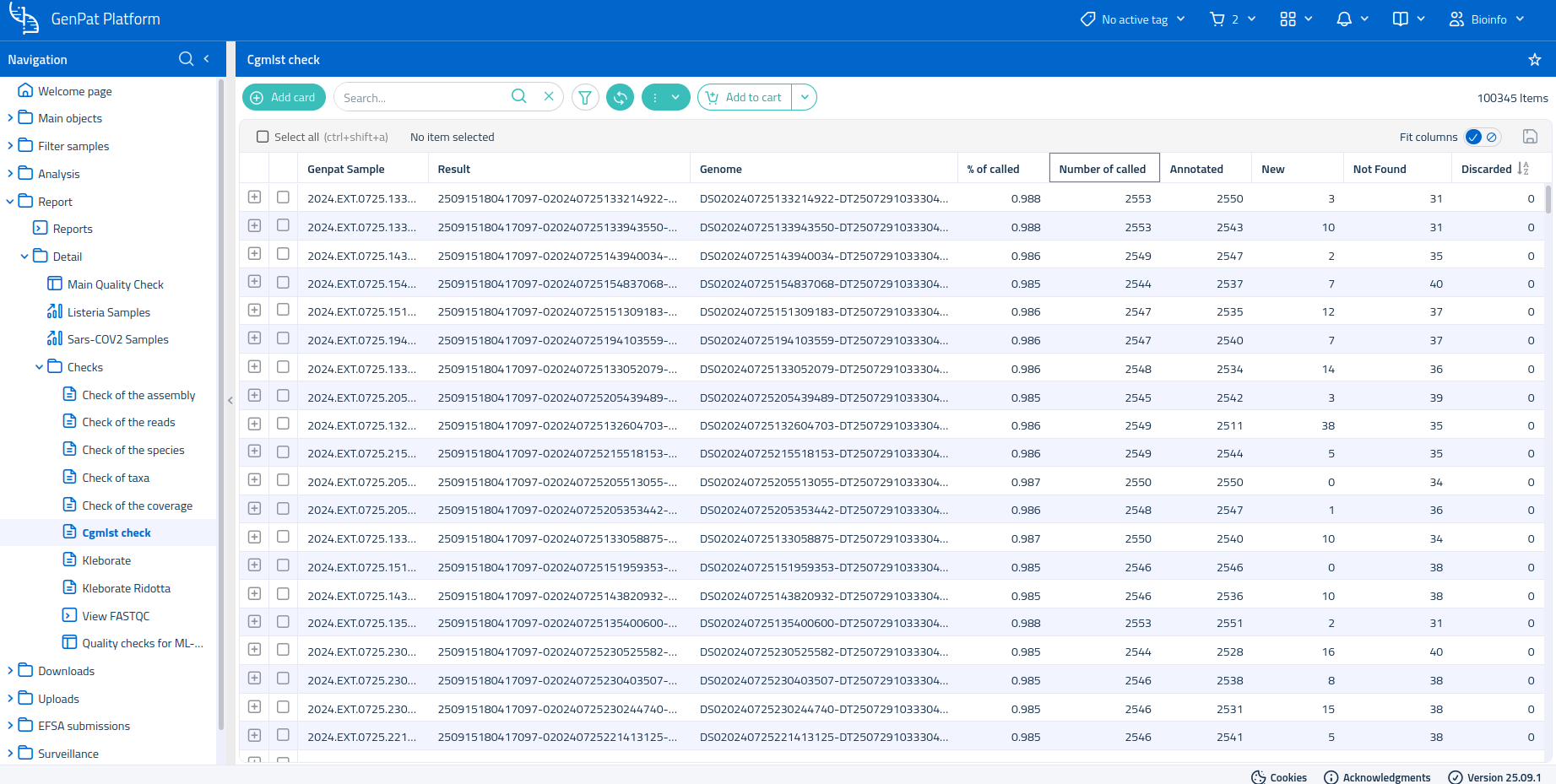
Le colonne dei metadati riportano il Codice dell'analisi e il codice del Campione a cui si riferiscono i dati. Le altre colonne elencano le statistiche aggregate degli alleli chiamati da chewBBACA (https://github.com/B-UMMI/chewBBACA): * % di chiamati: percentuale degli alleli chiamati da chewBBACA rispetto al totale dei loci nello schema; * Numero chiamati: numero degli alleli chiamati da chewBBACA; * Annotati, Nuovi, Non trovati, Scartati: ognuna di queste colonne riporta il numero di alleli in base a come sono stati chiamati o classificati da chewBBACA; - Annotati: varianti alleliche già presenti nello schema; - Nuovi: nuovi alleli, non presenti nello schema, ai quali sono stati assegnati dei nuovi codici; - Non trovati: (Locus Not Found - LNF), i loci che non sono stati trovati nel core genome del campione; - Scartati: loci per i quali la chiamata allelica non è sufficientemente affidabile.
Nota: il numero di loci dipende dallo schema di chewBBACA per lo specifico microrganismo.
