Pipeline NgsManager
Introduzione
La pipeline NgsManager permette la gestione delle reads e l'esecuzione di pipeline specifiche in base alla tipologia di campione.
Le pipelines eseguite da NgsManager sono le seguenti:
- pipeline Raw Read Processing - i risultati di 3TX_class__kraken nella pipeline Read Processing determinano l'identificazione di specie, in base alla quale vengono eseguite le analisi:
- Per batteri:
- pipeline WGS on Bacteria (esecuzione del de novo assembly con Shovill: step_2AS_denovo__shovill);
- pipeline Typing on Bacteria.
- Per virus:
- pipeline Vdraft (esecuzione del de novo assembly con Abricate: step_2AS_denovo__abricate + modulo Genome draft).
- Per SARS-CoV2:
(Per informazioni sulle singole analisi si consultino le pagine corrispondenti, raggiungibili cliccando sugli elementi sopra elencati).
Lancia la pipeline NgsManager
Nel sistema di lancio analisi, è possibile usare il filtro in alto per visualizzare esclusivamente le pipelines. Una volta selezionata la pipeline NgsManager nella pagina dedicata al lancio di analisi, il sistema passerà ad un'interfaccia di conferma.
La selezione delle pipelines di NgsManager, in caso di lancio manuale, avviene scegliendo la tipologia di campione, tra quelle disponibili, nella sezione di "Definizione parametri".
Per quanto riguarda l'input, NgsManager accetta:
- le raw reads (input step_0SQ_rawreads);
- step_1PP_trimming;
- step_1PP_hostdepl;
- step_1PP_generated;
- step_1PP_filtering;
- step_1PP_downsampling;
- step_2AS_mapping;
- step_2AS_indexing;
- file fasta importato (step_2AS_import).
Nel caso venga usato come input 2AS_mapping, sarà anche necessario un genoma reference, selezionato automaticamente dal sistema in base a quello usato per il mapping. La pipeline Raw read processing viene eseguita indistintamente per tutti i tipi di campione ma solo se l'input selezionato è costituito dalle raw reads.
L'interfaccia per la selezione dell'input mette anche a disposizione la modalità di selezione input avanzata, per permettere l'utilizzo di input processati da metodi diversi, usati a monte nel flusso di analisi.
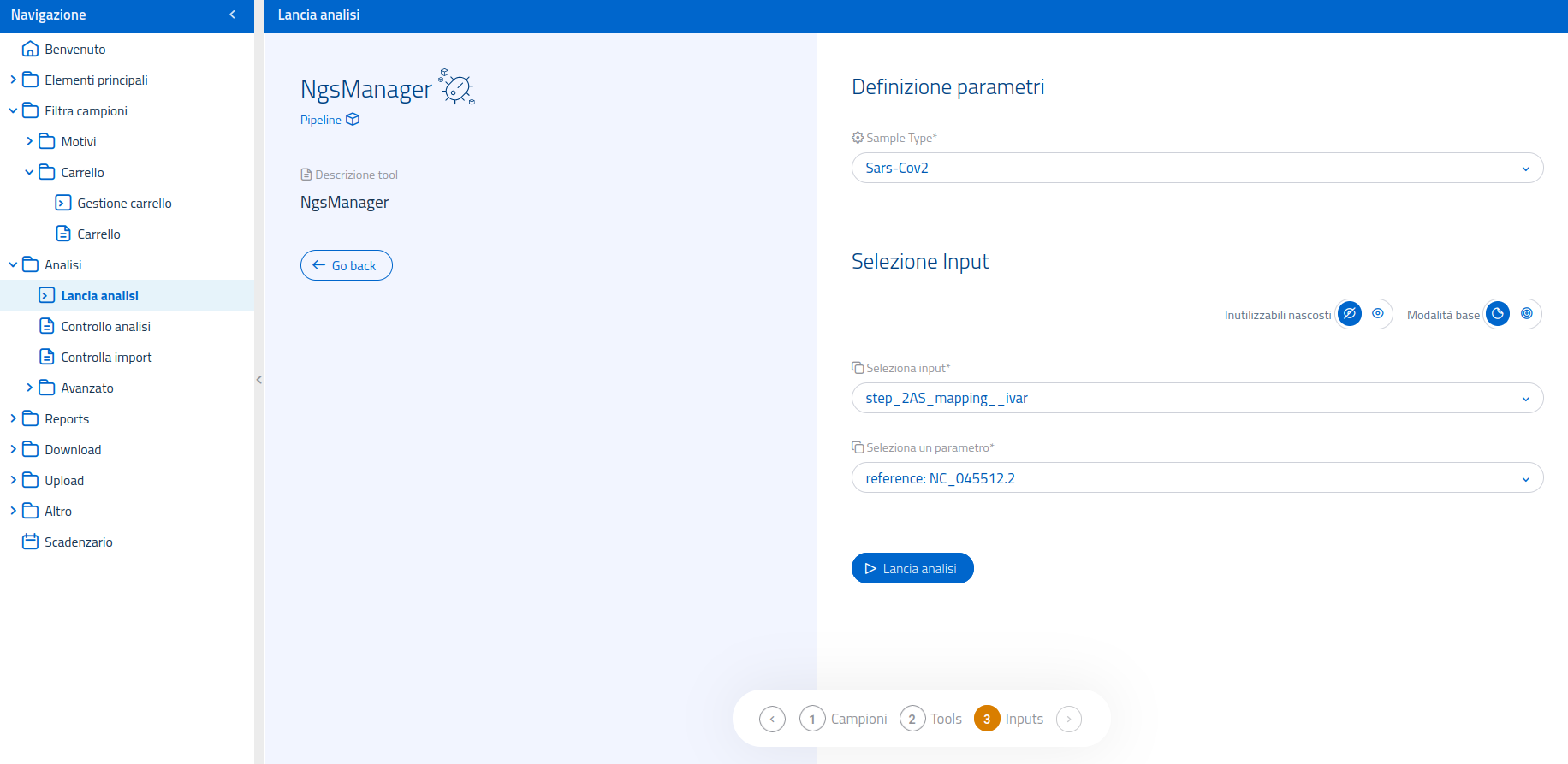
Una volta lanciata la pipeline, la pagina genererà un link alla sezione Controllo analisi, per permettere di visualizzare lo stato del processo. L'utente verrà notificato dal sistema sia una volta lanciata con successo la pipeline, sia al termine dell'esecuzione.
Risultati
I files prodotti da "NgsManager" dipendono dalle analisi che compongono le pipelines eseguite; essi sono organizzati con la stessa gerarchia usata per le analisi lanciate singolarmente. Come riferimento si rimanda quindi alle relative sezioni delle pipelines incluse in NgsManager, dove sarà possibile reperire tutte le informazioni riguardo le singole analisi e i link alle rispettive tabelle dei risultati.
