kSNP3
Introduzione
kSNP3 identifica i Polimorfismi a Singolo Nucleotide (SNPs) nei campioni, esegue un'analisi filogenetica senza allineamento (reference-free) e costruisce un albero filogenetico con algoritmo Maximum Likelihood (ML), a partire dalla matrice di SNPs dei campioni.
Una guida all'utente completa è disponibile nell'apposita sezione della guida di kSNP3.
Lancia Analisi kSNP3
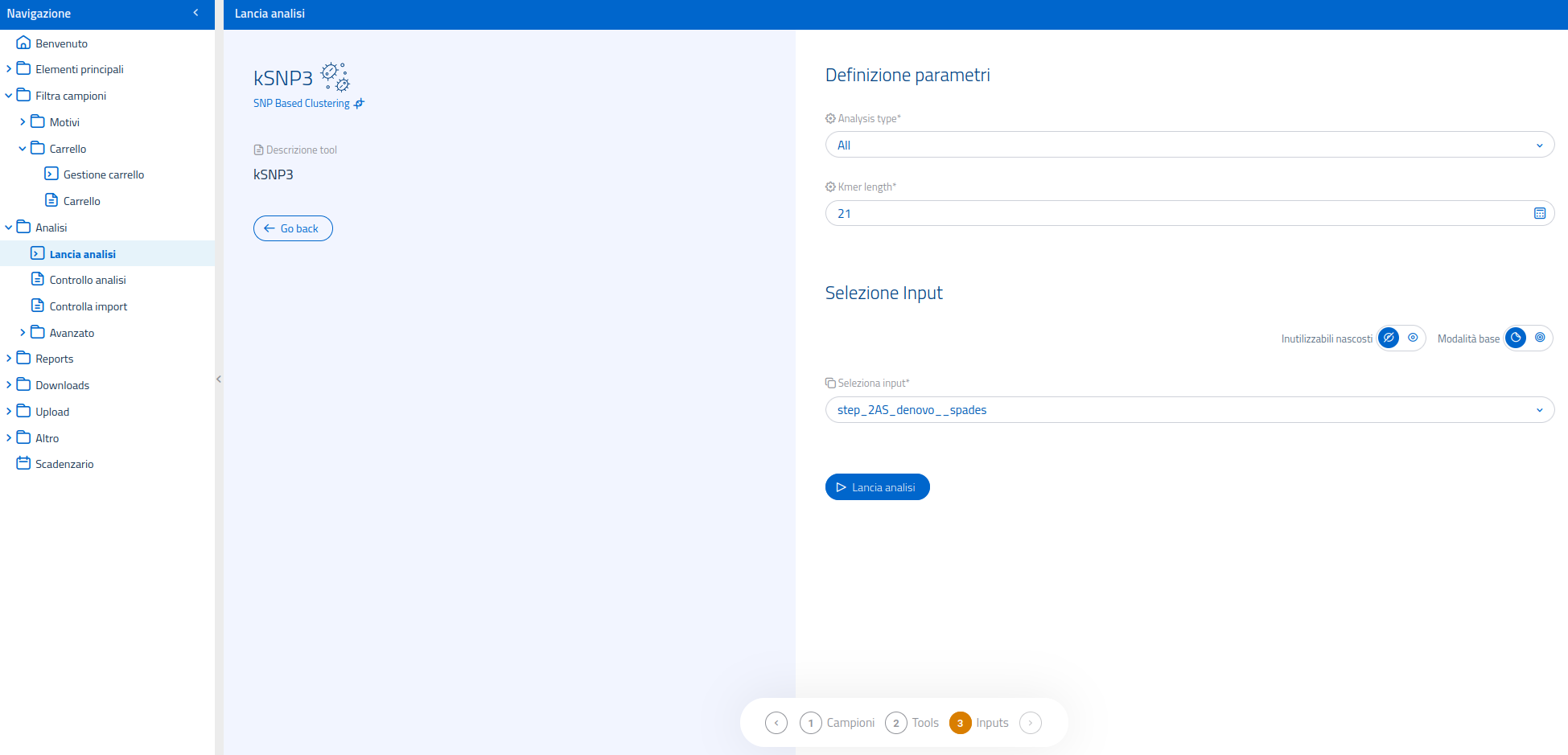
Una volta selezionata l'analisi kSNP3 nella pagina dedicata al lancio di analisi, il sistema passerà ad un'interfaccia di conferma dell'analisi scelta.
Nella sezione di definizione parametri sarà possibile scegliere se:
- effettuare l'analisi filogenetica utilizzando tutti gli SNPs ("All") o solo i Core SNPs (opzione "Analysis type");
- cambiare la lunghezza dei kmer (opzione "kmer length", default = 21).
L'interfaccia per la selezione dell'input mette a disposizione la modalità di selezione input avanzata, per permettere l'utilizzo di input processati da metodi diversi, usati a monte nel flusso di analisi.
Gli input utilizzabili per kSNP3 sono:
Una volta lanciata l'analisi, la pagina genererà un link alla sezione Controllo analisi, per permettere di verificare lo stato del processo. L'utente verrà notificato dal sistema sia una volta lanciata con successo l'analisi, sia al termine dell'esecuzione.
Dalla scheda dell'analisi completata è possibile, oltre all'esplorazione della cartella di output, anche la visualizzazione dell'albero .nwk e l'accesso diretto ad alcuni dei files di log e metadati.
Cartella dei risultati
Per consultare la guida sul download dei files dalla piattaforma si faccia riferimento all'apposita pagina.
La cartella dei risultati, Result folder, è accessibile cliccando sul link presente all'interno della scheda dell'analisi, nella sezione Dati risultato. All'interno della conseguente cartella results, è possibile trovare 2 sotto-cartelle:
- meta: ("metadati") in cui vengono salvati i file di log e di configurazione del processo eseguito.
- result: in cui sono salvati i file con i risultati prodotti dall'analisi.
Si tenga presente che, in base al parametro usato per Analysis type, il nome dei file di output sarà diverso:
- SNPs_all_matrix (se è stato selezionato "All" per Analysis type);
- core_SNPs_matrix (se è stato selezionato "Core" per Analysis type).
Nella tabella sottostante sono riportati i nomi nel caso di esecuzione su tutti gli SNPs ("All").
| File | Descrizione | Posizione |
|---|---|---|
| SNPs_all_matrix.fasta | file multifasta contenente gli headers con il nome del campione e la riga per la sequenza di SNPs concatenati. "N" indica l'assenza di uno SNP in quel campione | cartella "results" |
| SNPs_all_matrix.fasta.nwk | file dell'albero in formato nwk (newick) calcolato con algoritmo ML | cartella "results" |
Per ulteriori informazioni riguardo la formattazione degli output di kSNP3, si invita a consultare l'apposita sezione della guida utente kSNP3.
